副标题:通过重现Nature文献相关Figure掌握RNA-seq基本思路
先给答案:每天摸鱼10分钟,5小时了解转录组分析过程。每天学习1小时,30小时会跑转录组流程。每天3小时,100小时学会用已有工具做分析。
自从我参与的国内
第一篇植物高通量单细胞转录组文章
发表之后,就有很多人问我是如何学习生信的,是不是有专门的人教你?
了解我的人都知道,我的生信是被
逼
出来的。
当我进课题组的时候,就和老板说,我喜欢生信不想做实验,导师听完之后,也非常地支持我(
并且
温室不够用了
),于是就让我去摸索。随后我就发现实验室的高通量测序数据越来越多,测序类型也越来越丰富。看着这些数据,我能怎么办,只能努力学习呀。
学习最好的方式就是“
以教为学
”,在2年前的暑假,我非常详尽的更新了8篇转录组入门文章。到如今,只要你用“转录组入门”作为关键字进行搜索,那么你一定会在前几个搜索结果中看到一个作者叫做hoptop,那就是我。
最后我整理了一个专题,叫做转录组入门和进阶, 总阅读量也有10W+了。
今年我打算重新搞这种活动,带领大家至少能够
跑完
一次转录组项目。无论你之前是否有无经验,你都能够从头到尾跑完一次。
学习分为四周,每周各有一个主题。
-
第一周: Linux环境准备
-
第二周: 从原始数据到表达矩阵
-
第三周: 差异表达分析
-
第四周: 下游分析(GO/KEGG)
我们用于实战的文章是一篇Nature级别的文章,标题是Regulation of embryonic haematopoietic multipotency by EZH1
前言背景
人类外周血的造血细胞谱系都起源于造血干细胞,但是在哺乳动物胚胎中,却是谱系限制性祖细胞先出现,然后再出现造血干细胞。
研究表明,在小鼠胚胎发育的7.5天(yolk sac时期)就出现在红系髓系祖细胞及淋巴系祖细胞,而在10.5天的时候才出现造血干细胞,这个逆分化进程的造血现象目前还没有被很好的解释, 如今,美国哈佛医学院院长George Q. Daley提出猜想并论证了在胚胎发育早期存在表观沉默导致了抑制早期多能造血干细胞的出现。
文中论证了EZH1在造血早期起到的作用,并得到了EZH1在胚胎早期可以抑制细胞多能性这样的结论,文中使用了多种组学测序技术,包括:
-
RNA-seq
-
ChIP-seq
-
ATAC-seq
并且产出了一系列美观的图片,如下:
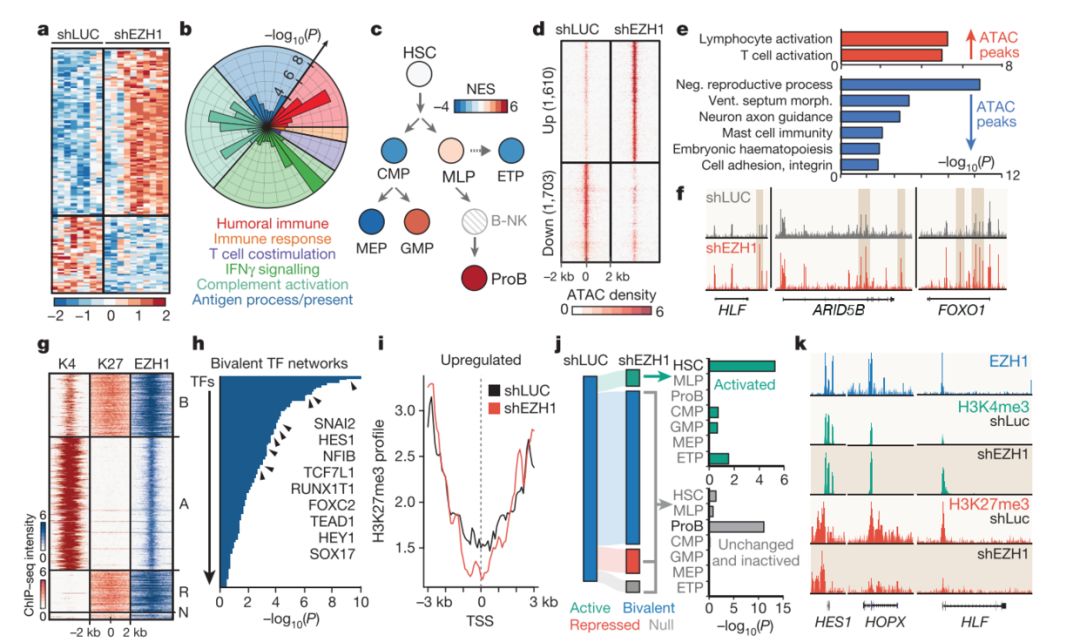
我们主要利用他们的RNA-seq数据,绘制热图,火山图,气泡图和GSEA等图。
文中的数据作者已经上传至GEO database,我们可以很方便的下载并进行处理
如何参与
我从下周一开始,连续四周,每周一会在生信媛发布任务和对应的学习资源,你所需要做的事情就是按照指南不断的学习。
因此理论上,你只要有一台笔记本电脑就可以自学了,因为学习所需要的资源网络上都有。但是能利用这些资源顺利入门的人并不多,不是不努力,而是最初的耐心和热情都在一个个报错中被消磨。
我们提供了一个
收费答疑群
,定价为299,发放
讲解视频
,耐心解答实战过程中你会遇到的问题。
加群方式,扫描二维码加我好友,之后转账299,我拉你进学习群。

最终通过本次课程,你可以
学到
:




