前言:
在上一次文章中,
CRISPR/Cas9基因编辑之背景介绍及gRNA设计
我们已经得到了在线工具设计的sgRNA序列,经由简单评估后选择出合适的sgRNA
现在我们来模拟质粒的的构建过程并且设计一对引物用于基因编辑的结果检测
1. 使用Snapgene anneal oligo
以上一次文章查到的PTEN knockout cell line 为案例,根据给出的PTEN sgRNA,完善oligo序列,并再Snapgene软件中匹配出来

使用Snapgene一键生成oligo,Actions--Anneal Oligos
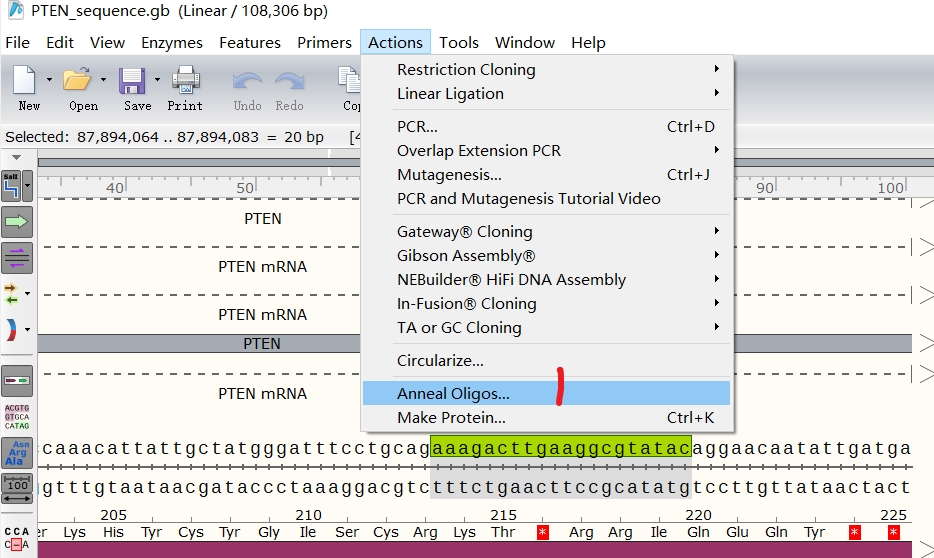
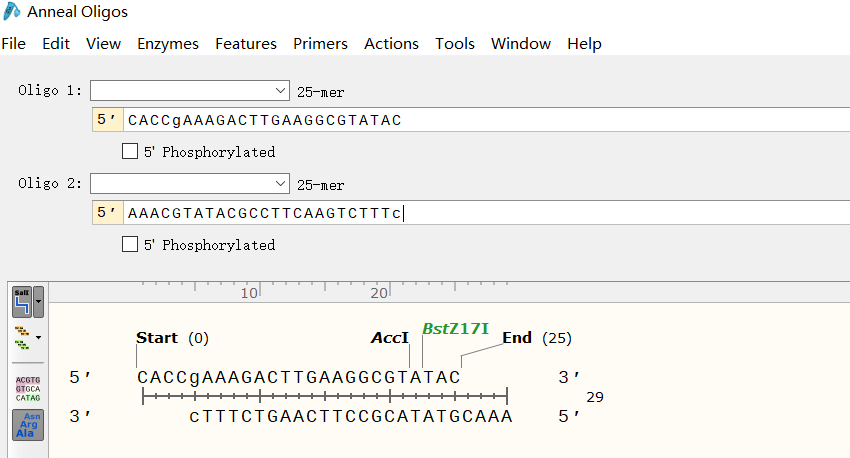
粘贴事先准备好的序列--保存Oligo文件
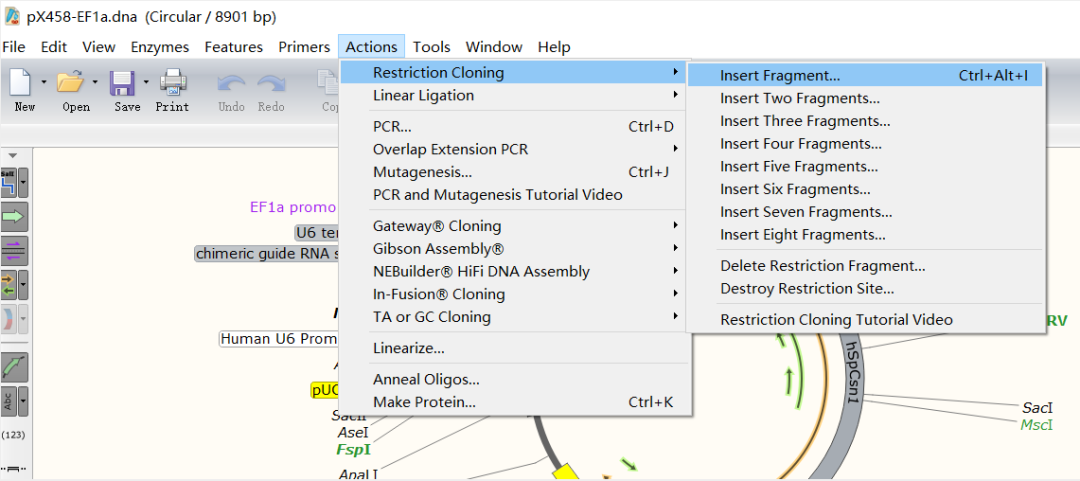
2. 使用Snapgene模拟插入质粒后的情况
(1)打开一个pSpCas9质粒--actin--restriction cloning--insert fragment
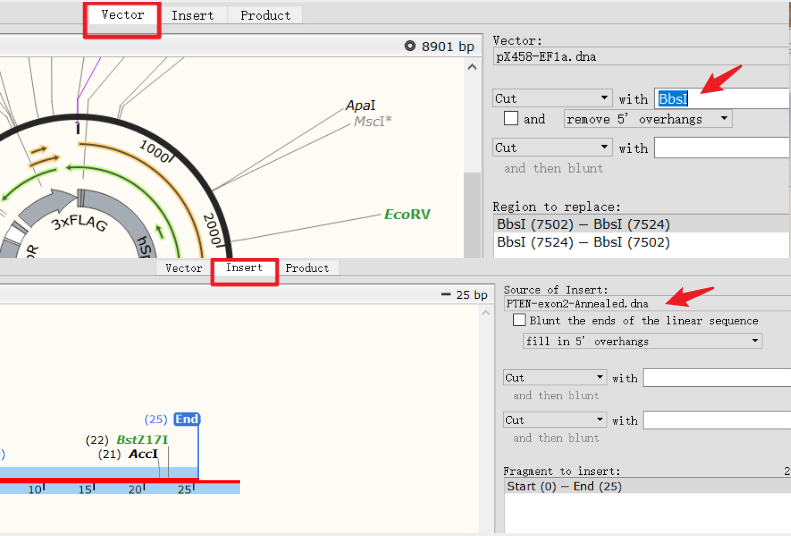
(2)在Vector选项卡,选择内切酶为BbsI,在insert部分选择上一步中保存好的oligo,最后点击clone,保存DNA文件。
(3)打开插入后的质粒图谱,检查oligo插入情况,无误后可提交上表中的PTEN-Oligo.Top/Bottom至公司合成。
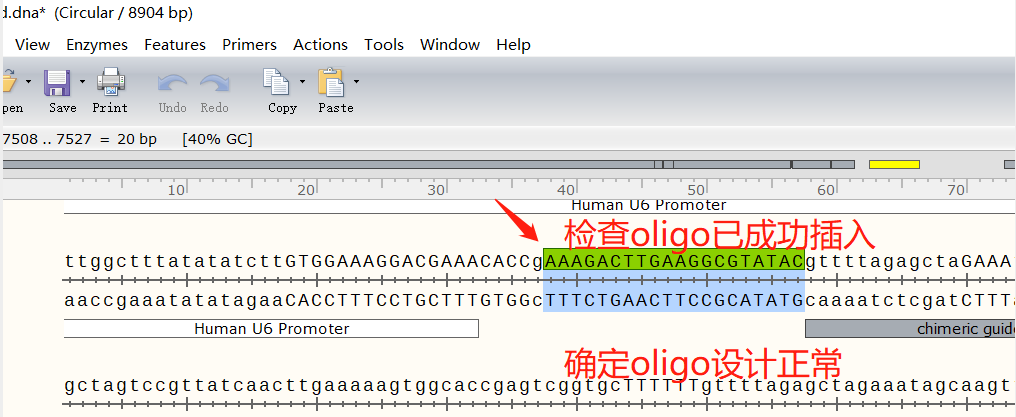
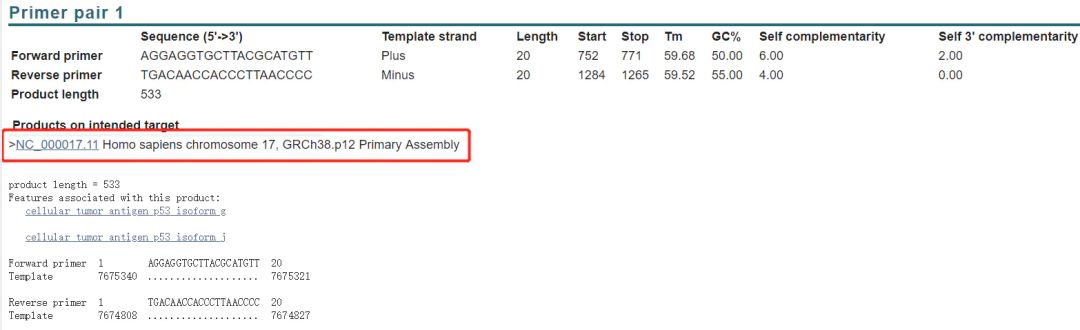
3. 设计检测所需引物
这里检测所用的引物和平时做PCR检测mRNA表达的引物是不同的,这里的PCR产物必须覆盖基因编辑的位置,用于基因编辑完成后的检测,产物要足够长,至少500 bp。
在这里我们以P53为例子:
(1)找到包括sgRNA序列的前后1000个碱基的序列(2000 bp)
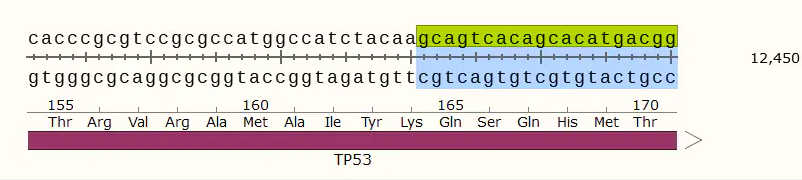
(2)将找到的序列复制粘贴到blast中
https://www.ncbi.nlm.nih.gov/tools/primer-blast/
设置参数
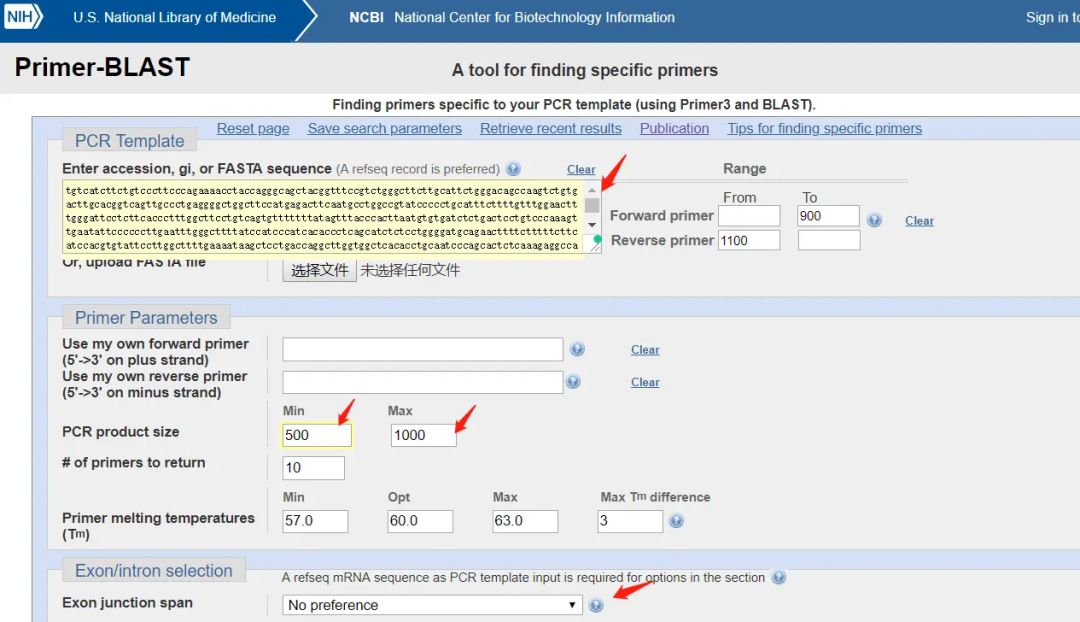
(3)得到结果)
(小测试,为何得到的引物只有两对,而且似乎有一对还偏离中心很远,请问应该如何设置,使得产物聚集在中心?
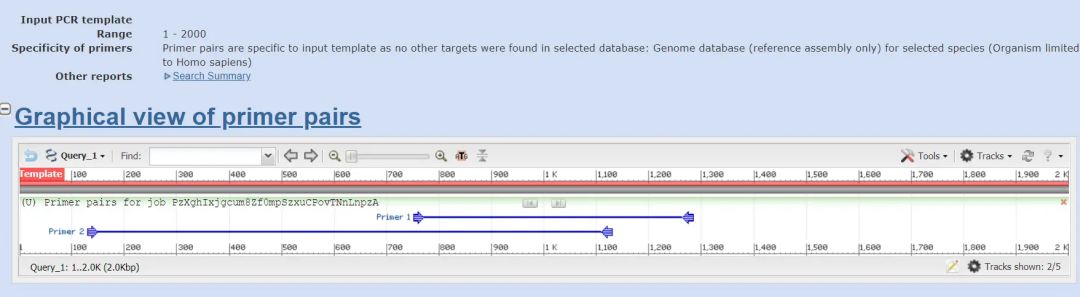
(4)查看引物基本情况,检查无误可提交公司合成
结语:
以上,我们则是完成了sgRNA及引物设计,提交公司合成,拿到之后则可开始正式实验了,感兴趣的同学,可以完成上面的小测试,有问题请在下方留言,拜拜~





