
对大家来说,我们常常面临的一个问题就是:如何根据自己关心的疾病或者研究主题选择信号通路以及分子,今天我们先来介绍一个网站来解决这个问题。
网站名字叫
WikiPathway
:http://www.wikipathways.org
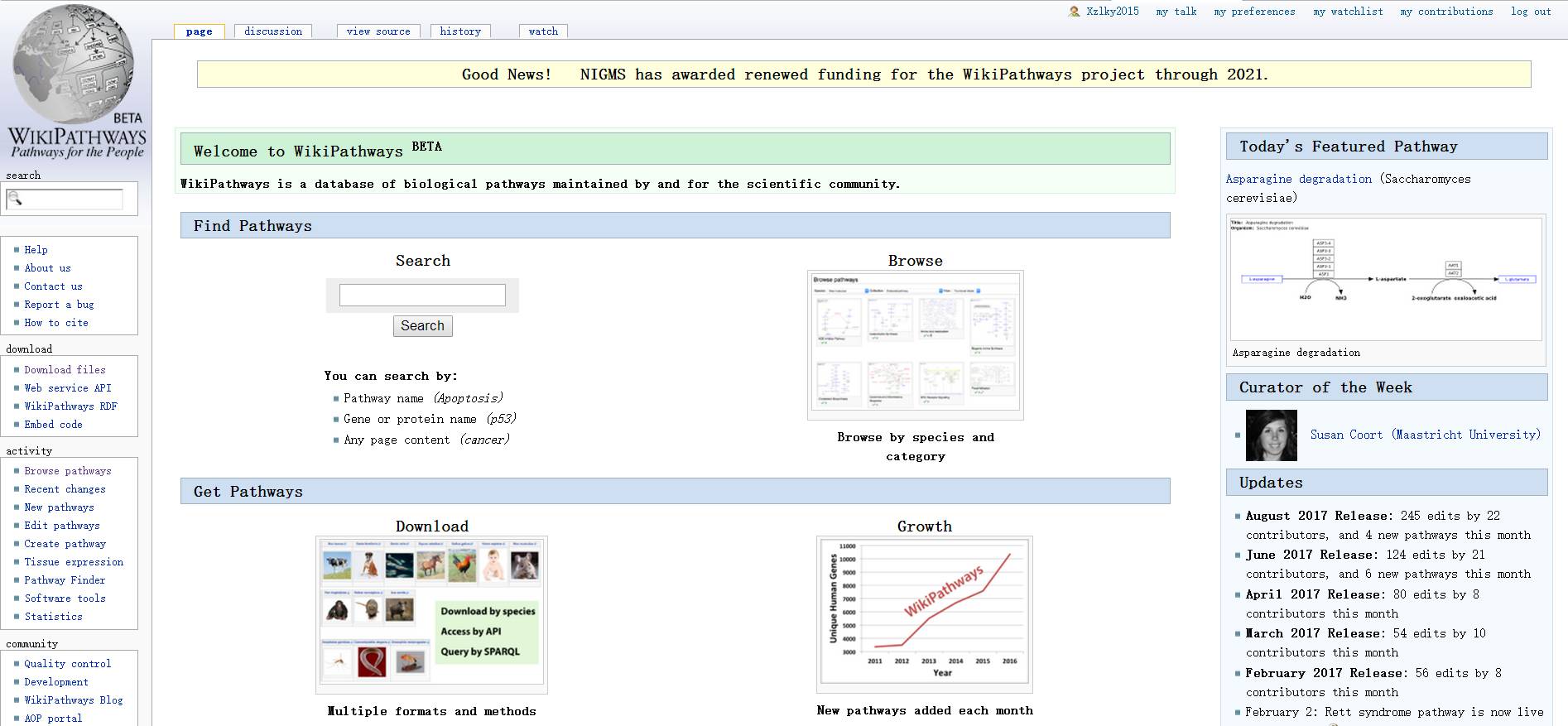
上面是文章的主页,我们可以搜索也可以浏览相关的通路,比如我们想看与心脏发育有关的通路和分子,在Search这个搜索框中输入heart development就好了:
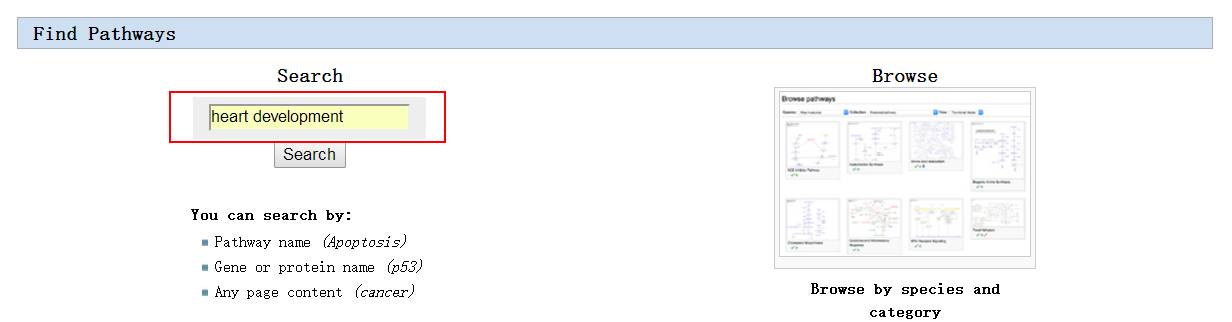
这是出来的结果:
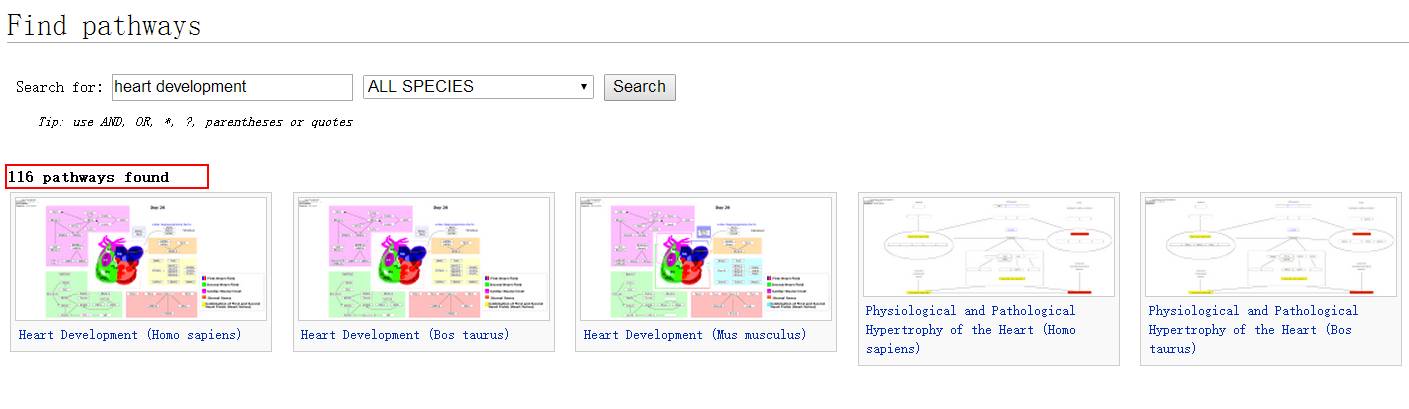
这里我们就看到了116条相关的通路,其中不仅有人类的,还有牛和小鼠的:
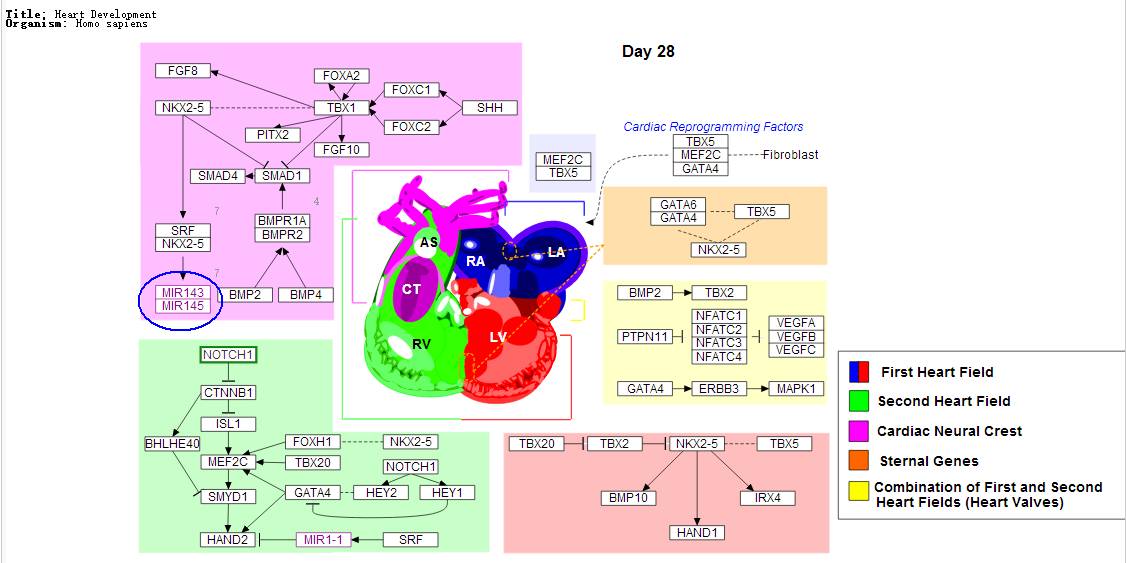
这个是人心脏发育有关的通路,我们看到这个列表里面不仅有基因的,还有miRNA的名字(蓝框标注)。另外,页面下面是这条通路中的基因:
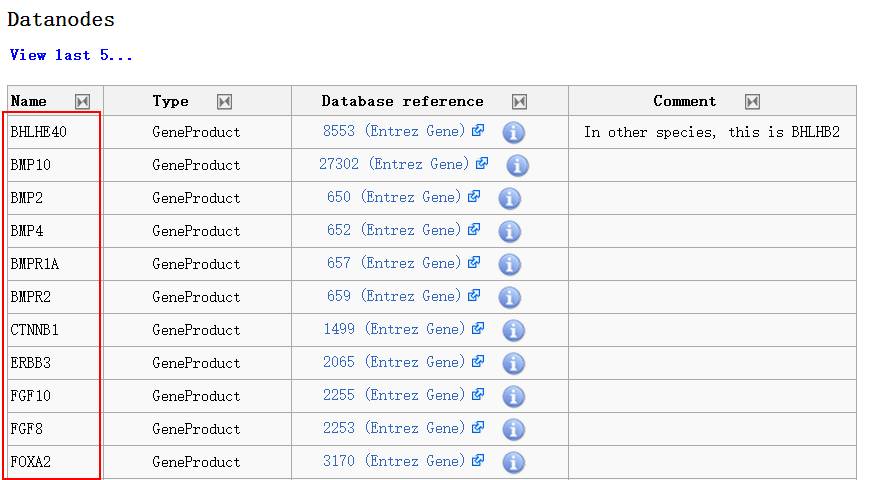
这个是搜索功能,简单好用。
下面我们接着来介绍另外一个功能:
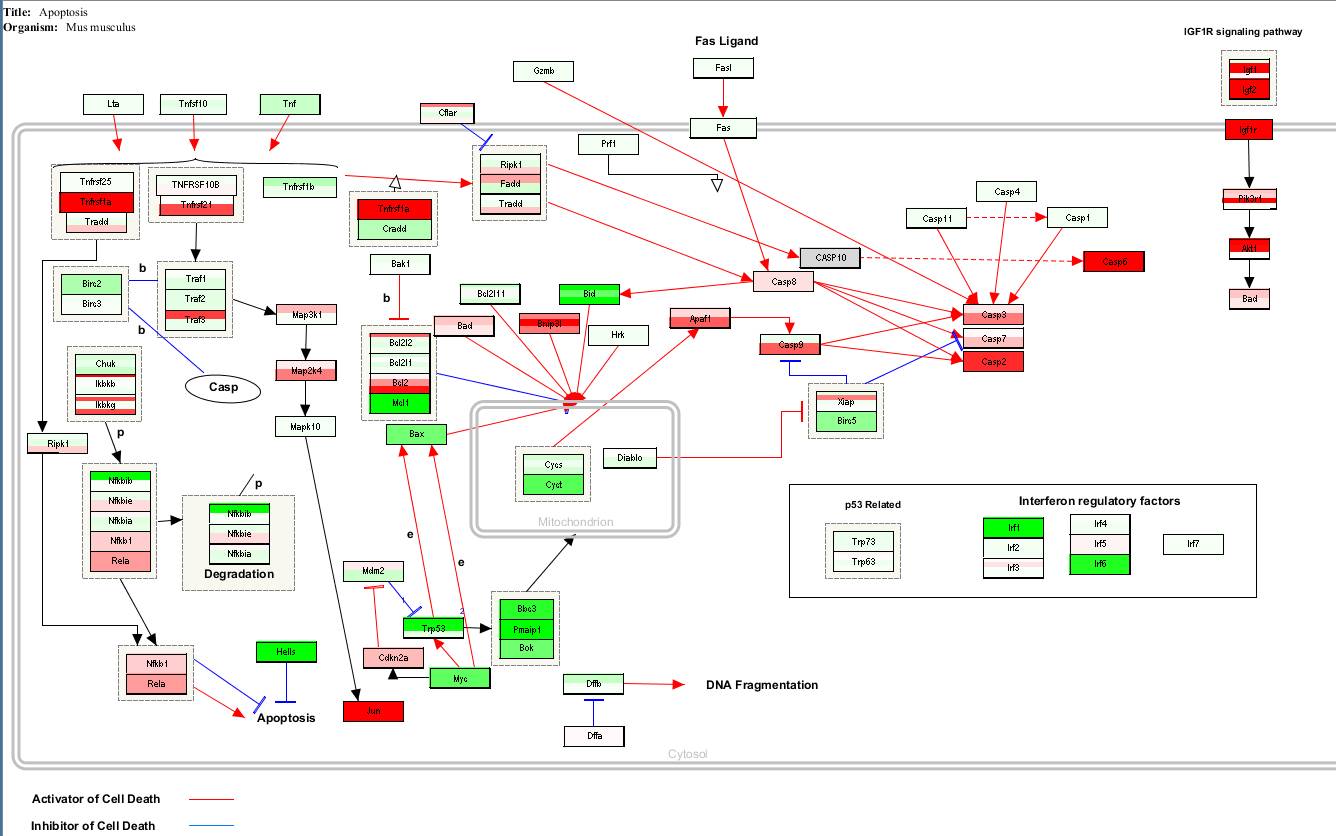
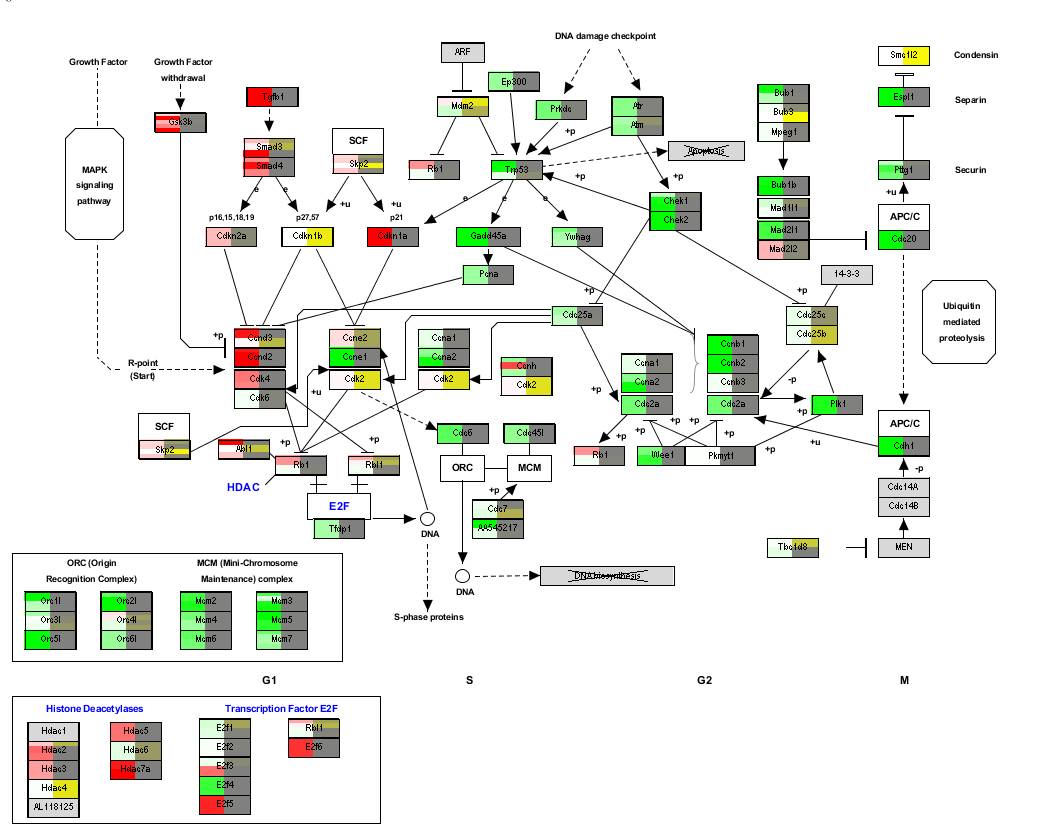
如何把基因表达的结果在信号通路图里面标注出来
,即自己绘制下面的图:
使用的工具是Pathvisio:
下载地址:
https://www.pathvisio.org/downloads/,下载安装后这是主界面:
我们需要使用一个文件
tutorial_files
下载链接:
http://www.pathvisio.org/data/tutorials/tutorial_files.zip
这个是文件的内容:
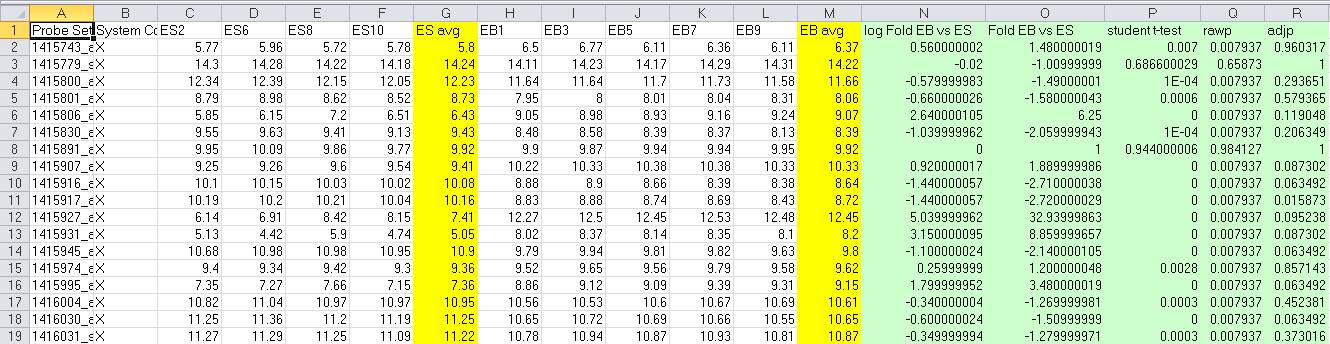
excel文件的内容是基因的表达结果:
接下来我们把excel保存为txt格式的文本文件:
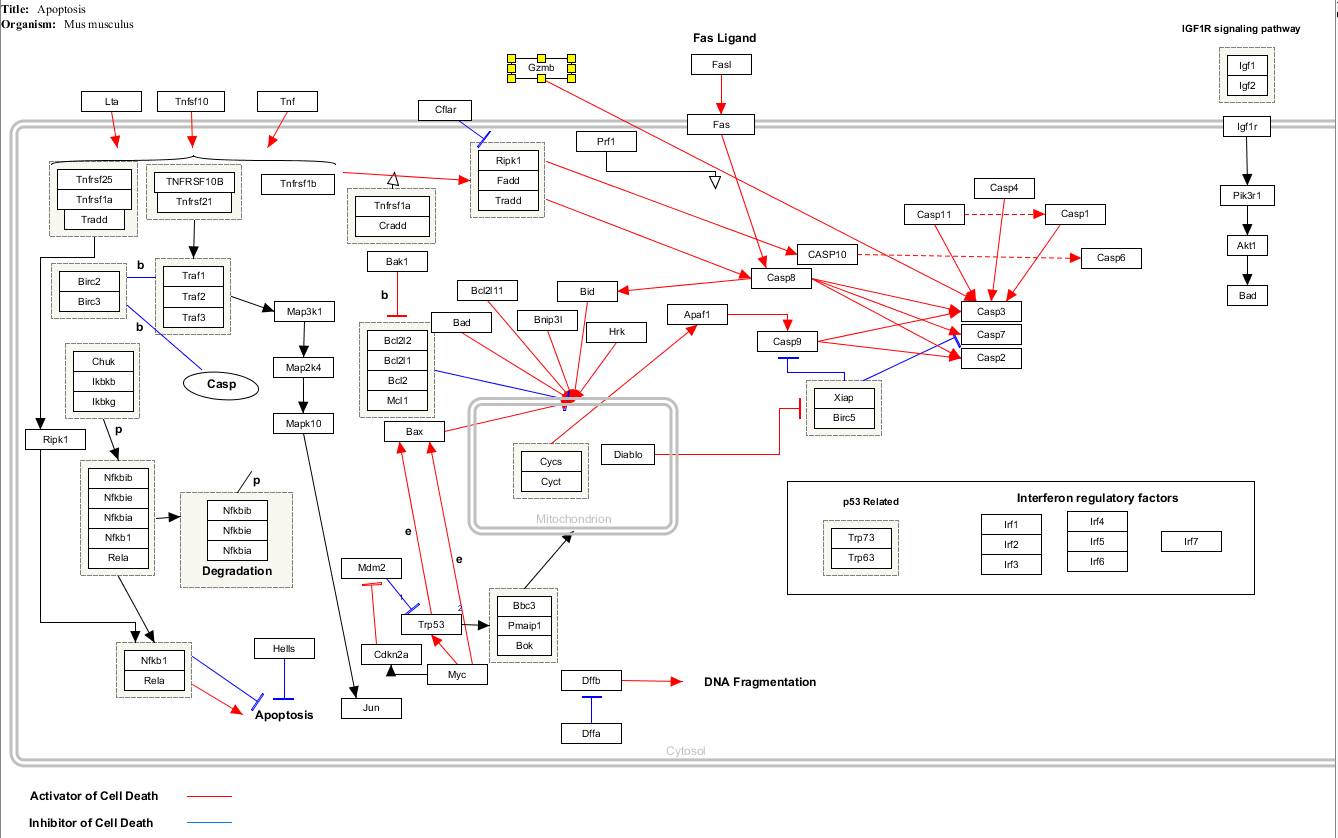
下面我们首先打开通路:
file——
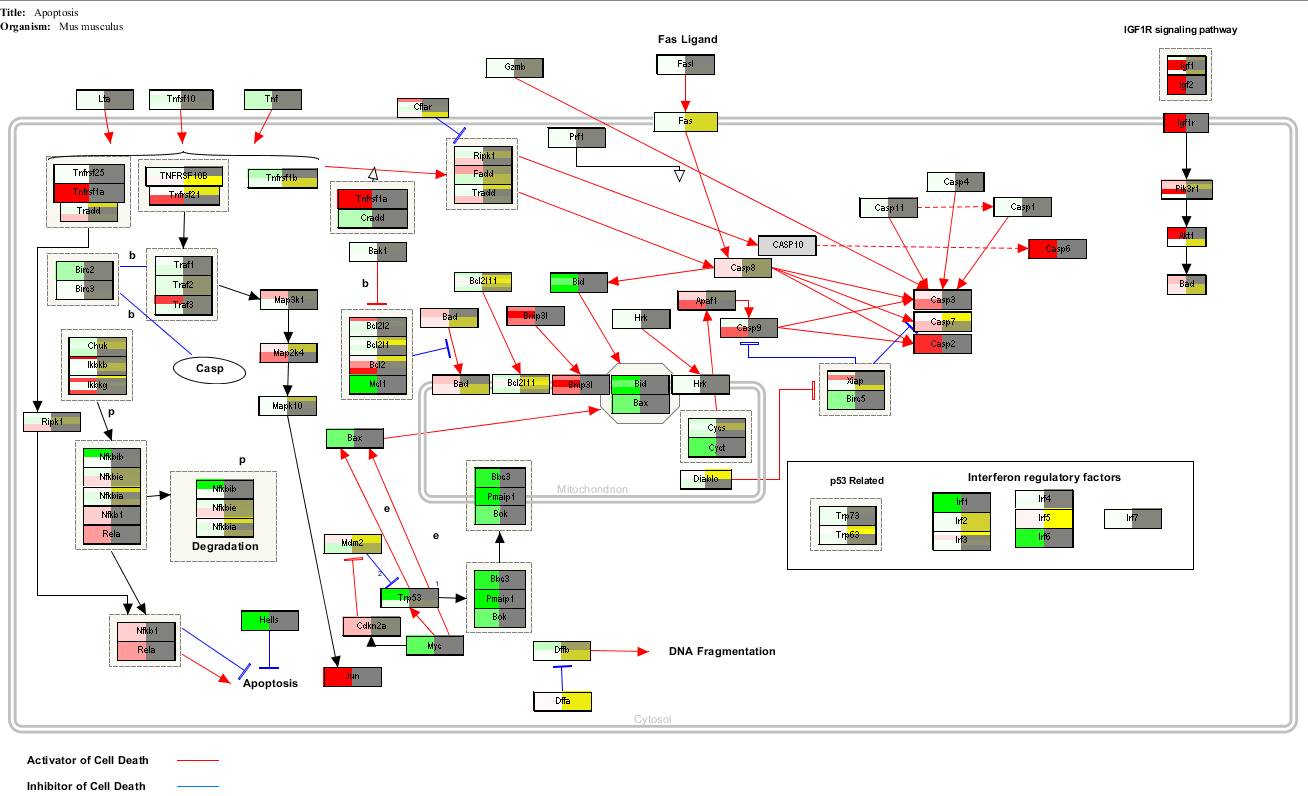
open,选择Mm_Apoptosis.gpml文件,是这样的:
然后我们把表达的数据导入:
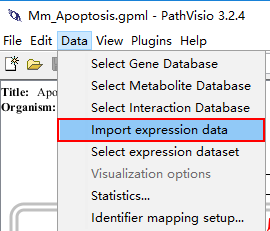
然后选择刚才转换的txt文件,Gene database选择Mm_lite.pgdb文件:
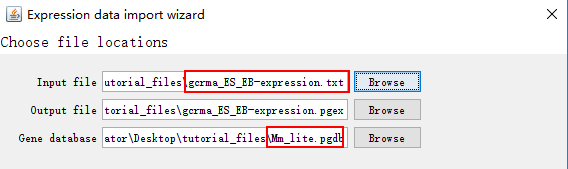
接下来的操作默认选择即可,最后的界面:
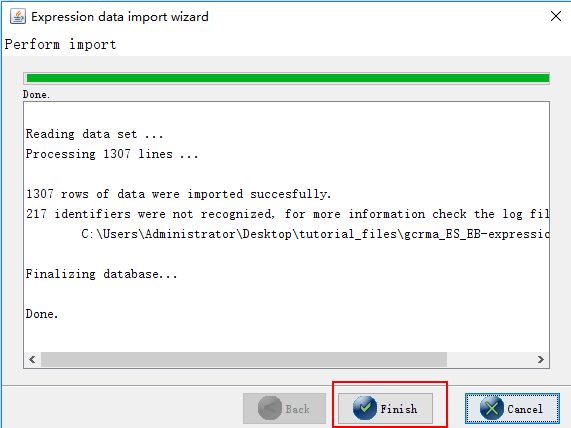
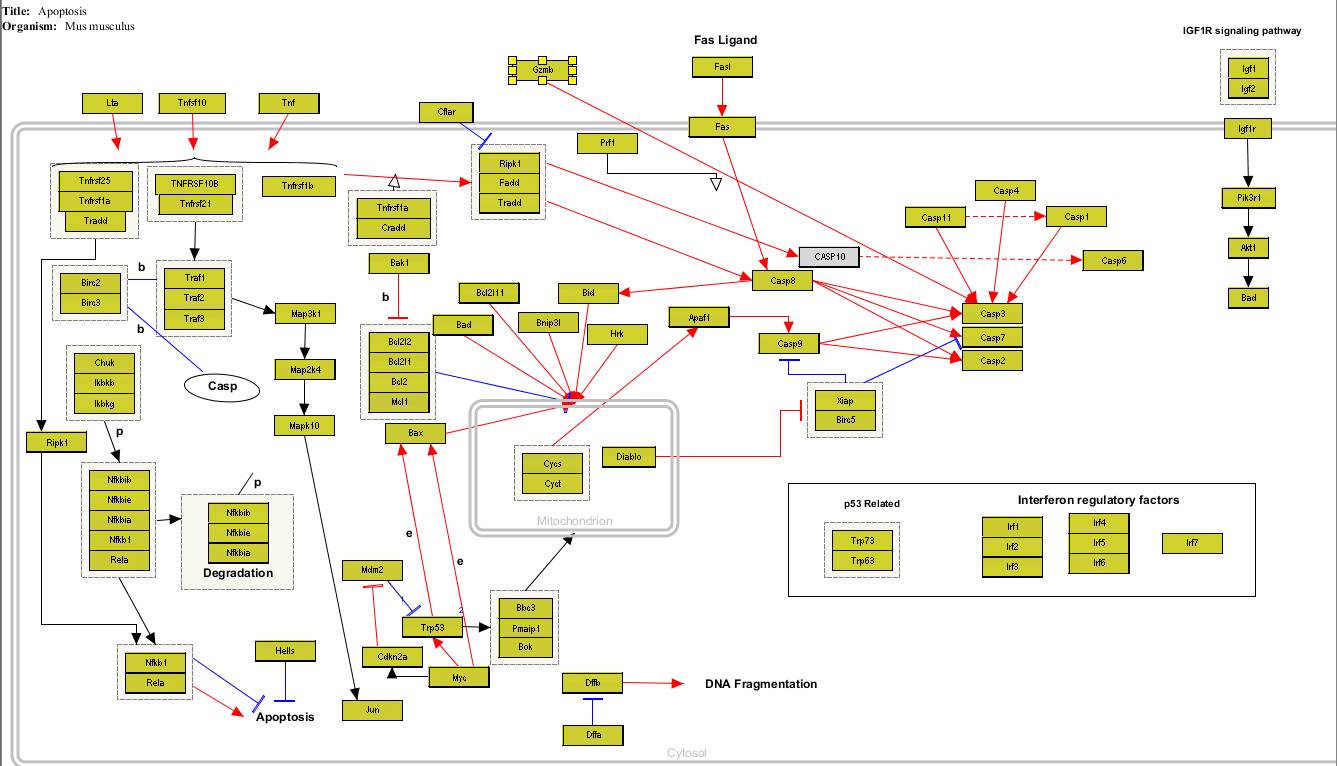
一共识别了1307个基因,对应的通路图也变成了这样:
接下来我们进行设置:Data-Visualization options:
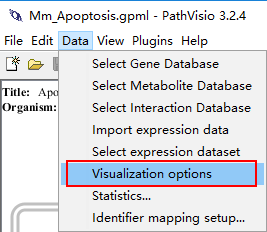
重点来了:在下面的候选框里面选择log Fold EBvsES,是EB和ES
两组的表达倍数结果,然后在color set右侧的下三角处选择modify:
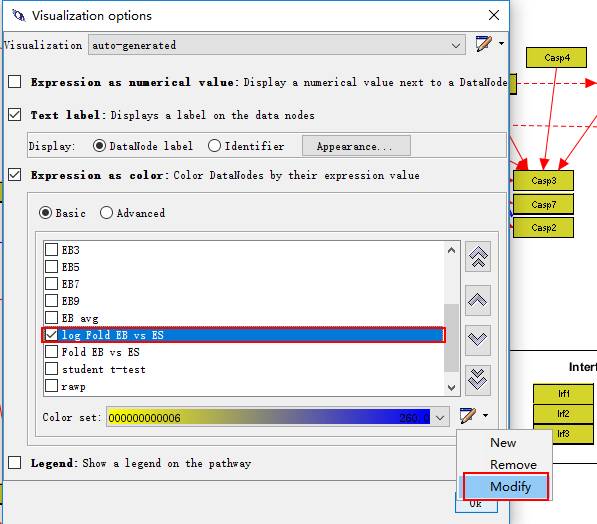
选择红绿色显示:
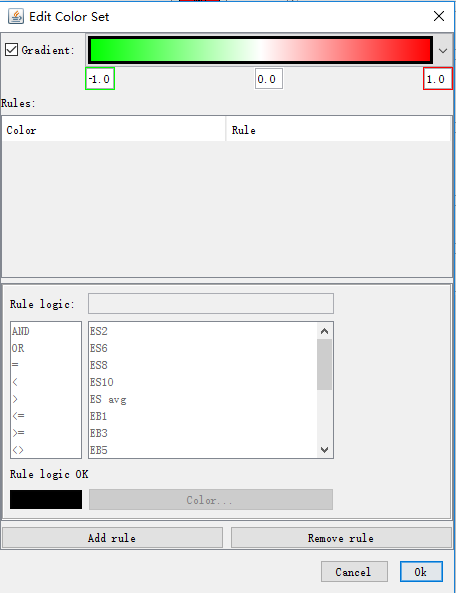
单击OK后就变成这样了:
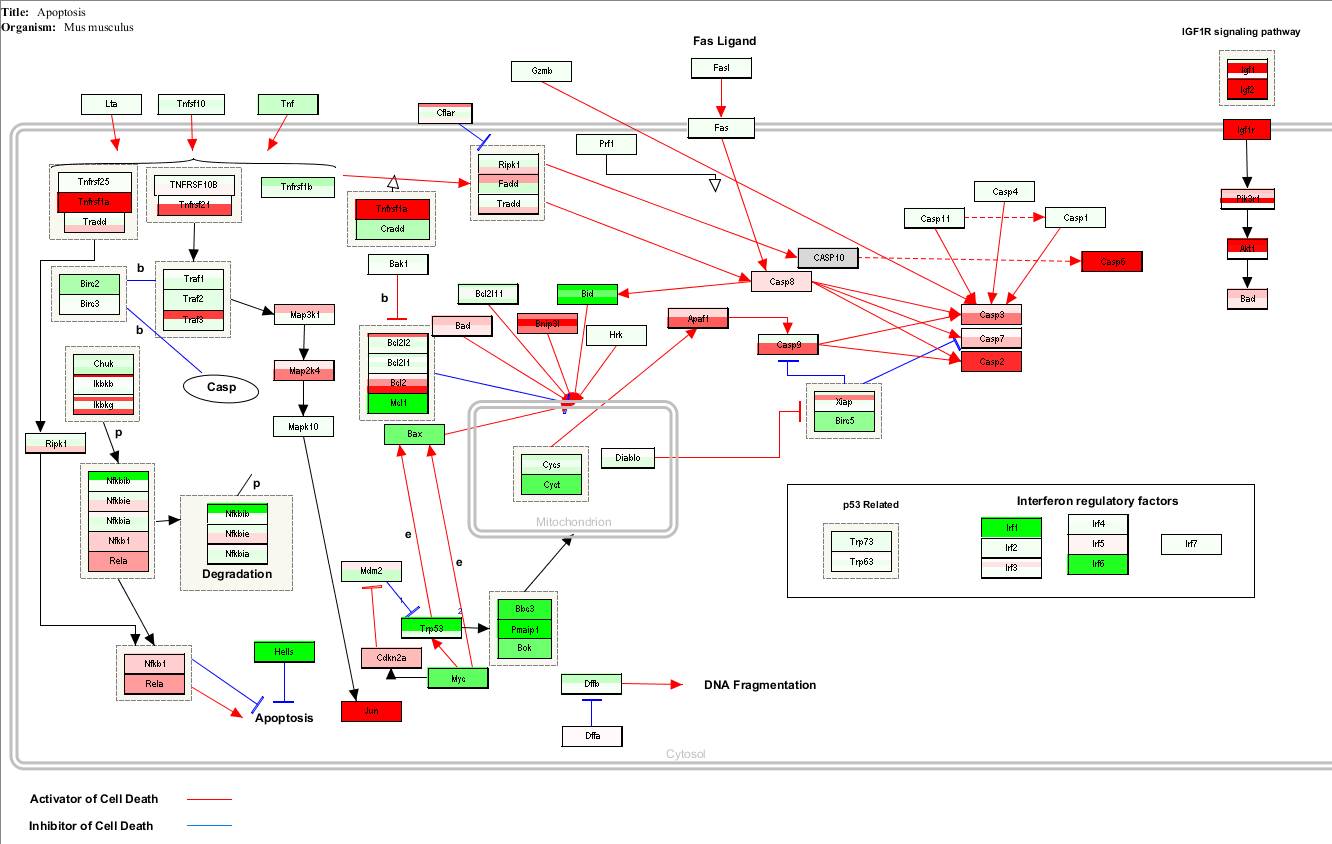
这里我们标注的是基因表达的倍数在通路里面的结果,其中一个基因出现多个颜色是因为多条探针对应到这个基因,而这些探针的结果则是不同的。
当然还可以标注P值和校正的P值:
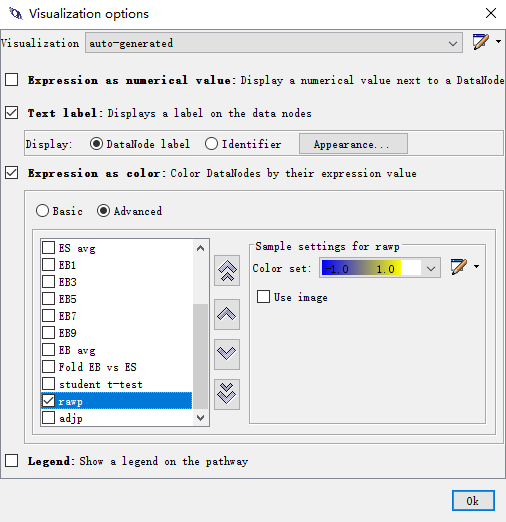
通路图就变成这样了:
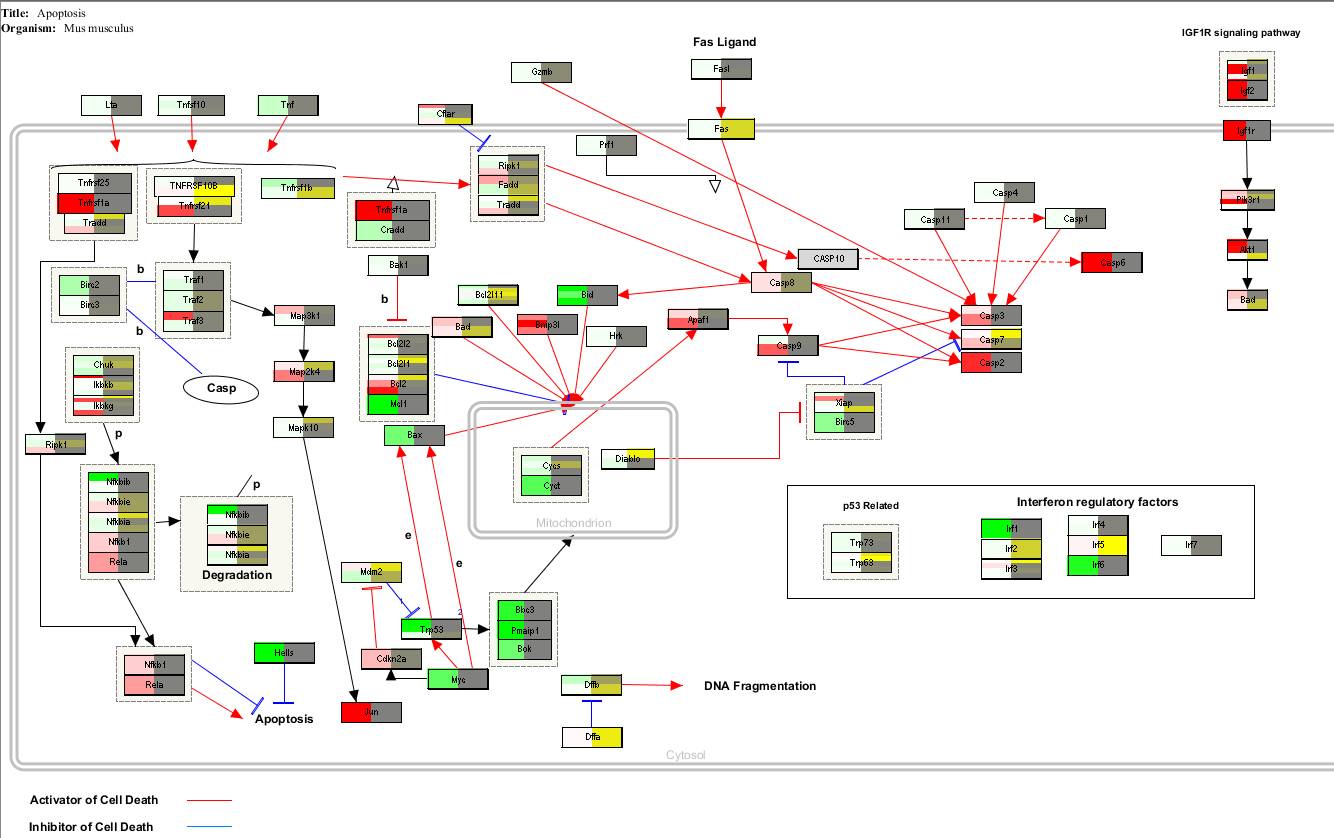
左侧的红绿图是倍数,右侧的蓝黄色是P值。
最后,我们安装PathVisio的插件后还可以直接看各种通路图:
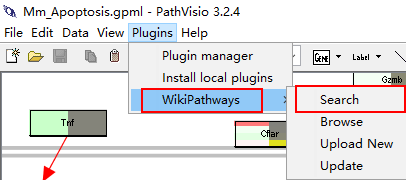
小鼠里面与细胞周期cell cycle相关的通路找到87条:
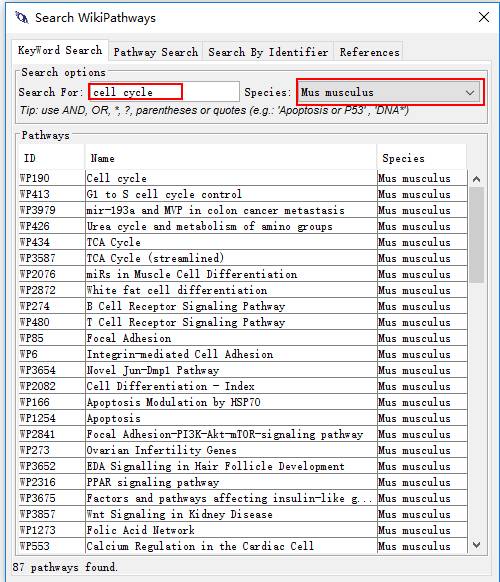
可以直接双击查看:
长按二维码识别关注“小张聊科研”

关注后获取《科研修炼手册》1、2、3、4、5,基金篇、生信特辑





