上篇文章中提了一下如何通过
ggpubr
包为
ggplot
图添加
p-value
以及显著性标记,本文将详细介绍。利用数据集
ToothGrowth
进行演示
#先加载包
library(ggpubr)
#加载数据集ToothGrowth
data("ToothGrowth")
head(ToothGrowth)
## len supp dose
## 1 4.2 VC 0.5
## 2 11.5 VC 0.5
## 3 7.3 VC 0.5
## 4 5.8 VC 0.5
## 5 6.4 VC 0.5
## 6 10.0 VC 0.5
比较方法
R
中常用的比较方法主要有下面几种:
|
方法
|
R函数
|
描述
|
|
T-test
|
t.test()
|
比较两组(参数)
|
|
Wilcoxon test
|
wilcox.test()
|
比较两组(非参数)
|
|
ANOVA
|
aov()或anova()
|
比较多组(参数)
|
|
Kruskal-Wallis
|
kruskal.test()
|
比较多组(非参数)
|
各种比较方法后续有时间一一讲解。
添加
p-value
主要利用
ggpubr
包中的两个函数:
compare_means()
函数
该函数主要用用法如下:
compare_means(formula, data, method = "wilcox.test", paired = FALSE,
group.by = NULL, ref.group = NULL, ...)
注释:
-
formula
:形如
x~group
,其中x是数值型变量,
group
是因子,可以是一个或者多个
-
data
:数据集
-
method
:比较的方法,默认为
"wilcox.test"
, 其他可选方法为:
"t.test"
、
"anova"
、
"kruskal.test"
-
paired
:是否要进行
paired test
(
TRUE
or
FALSE
)
-
group_by
: 比较时是否要进行分组
-
ref.group
: 是否需要指定参考组
stat_compare_means()
函数
主要用法:
stat_compare_means(mapping = NULL, comparisons = NULL hide.ns = FALSE,
label = NULL, label.x = NULL, label.y = NULL, ...)
注释:
-
mapping
:由
aes()
创建的一套美学映射
-
comparisons
:指定需要进行比较以及添加
p-value
、显著性标记的组
-
hide.ns
:是否要显示显著性标记ns
-
label
:显著性标记的类型,可选项为:
p.signif
(显著性标记)、
p.format
(显示
p-value
)
-
label.x
、
label.y
:显著性标签调整
-
…:其他参数
比较独立的两组
compare_means(len~supp, data=ToothGrowth)
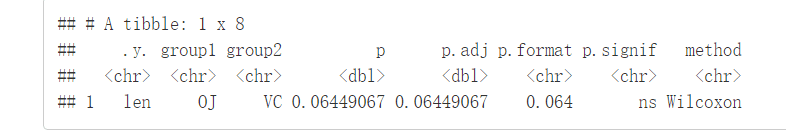
结果解释:
-
.y
:测试中使用的y变量
-
p
:
p-value
-
p.adj
:调整后的
p-value
。默认为
p.adjust.method="holm"
-
p.format
:四舍五入后的
p-value
-
p.signif
:显著性水平
-
method
:用于统计检验的方法
绘制箱线图
p
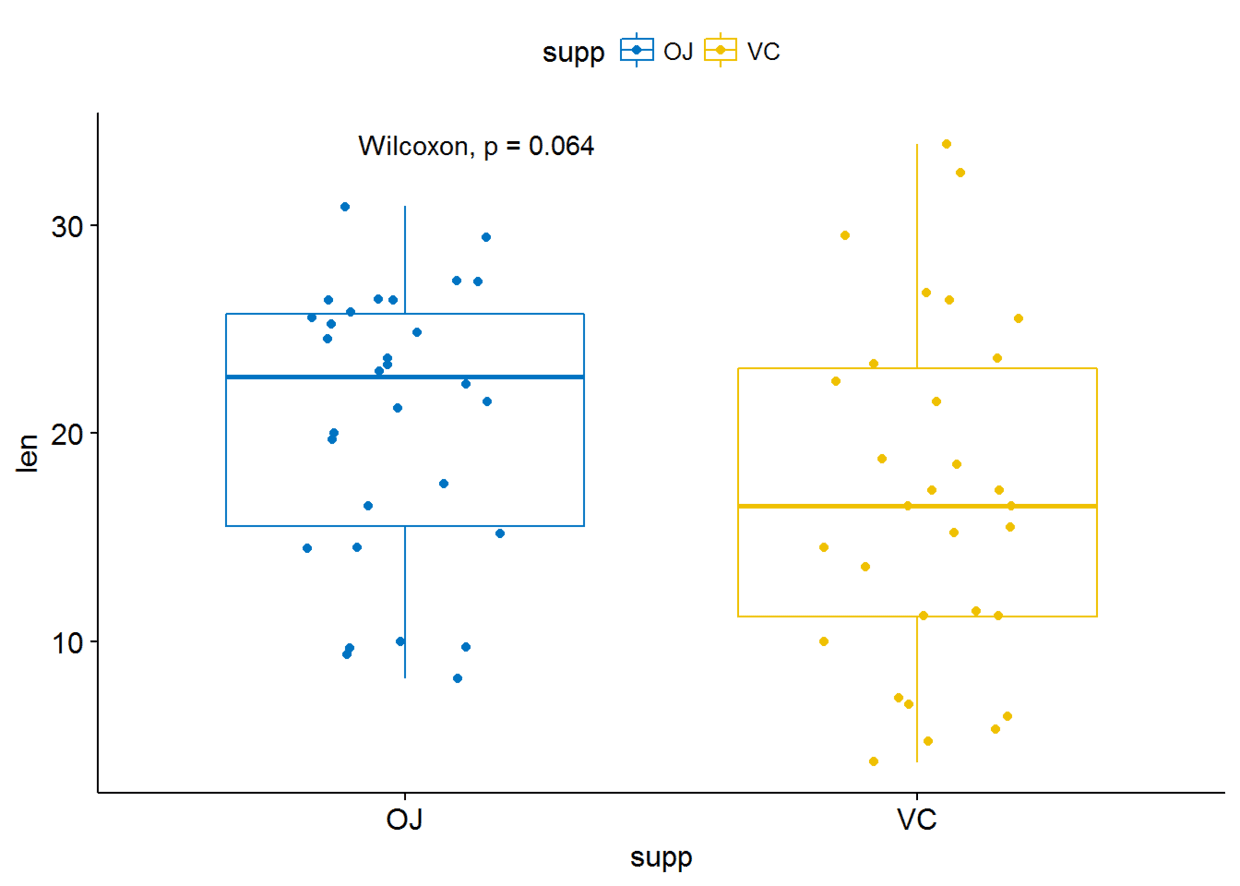
#使用其他统计检验方法
p+stat_compare_means(method = "t.test")

上述显著性标记可以通过
label.x
、
label.y
、
hjust
及
vjust
来调整
显著性标记可以通过
aes()
映射来更改:
-
aes(label=..p.format..)
或
aes(lebel=paste0("p=",..p.format..))
:只显示
p-value
,不显示统计检验方法
-
aes(label=..p.signif..)
:仅显示显著性水平
-
aes(label=paste0(..method..,"\n", "p=",..p.format..))
:
p-value
与显著性水平分行显示
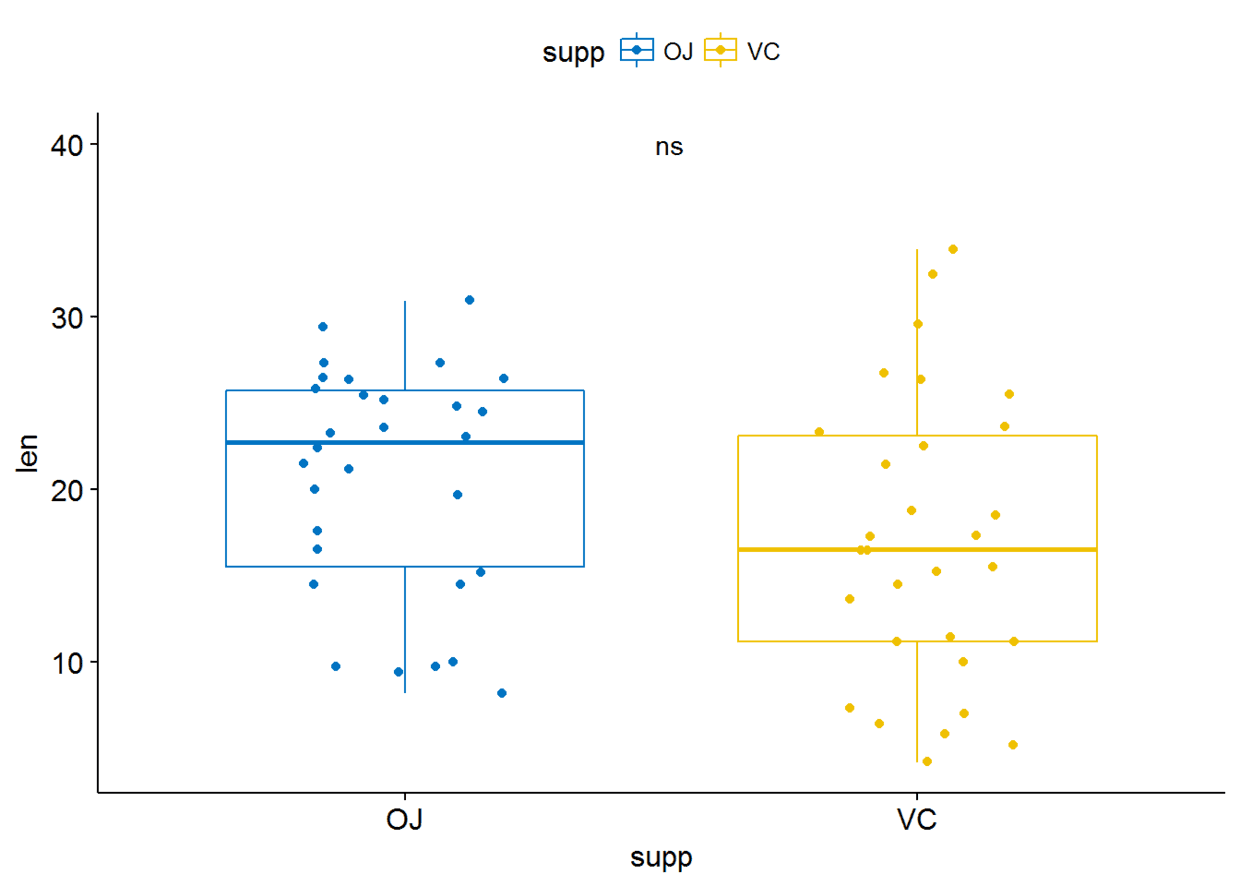
举个栗子:
p+stat_compare_means(aes(label=..p.signif..), label.x = 1.5, label.y = 40)
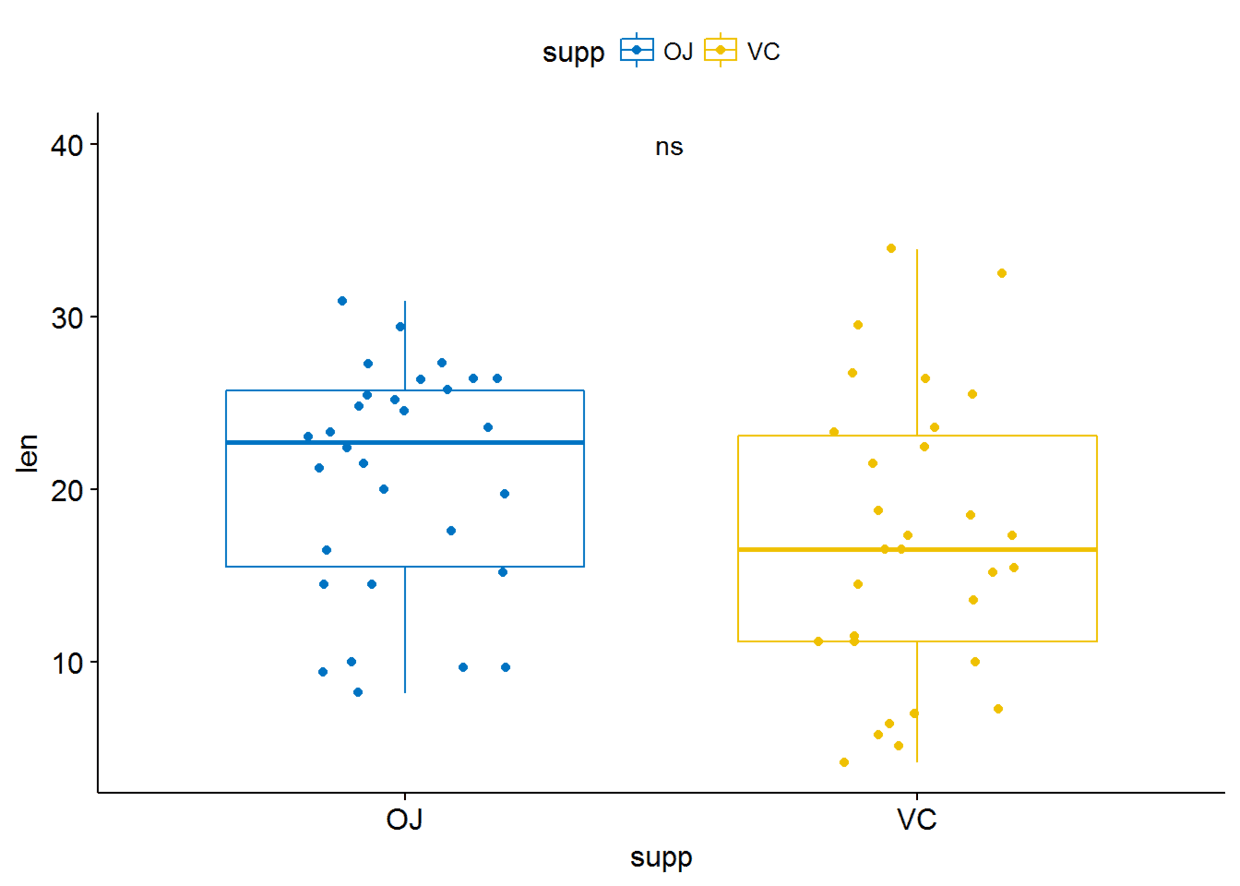
也可以将标签指定为字符向量,不要映射,只需将p.signif两端的..去掉即可
p+stat_compare_means(label = "p.signif", label.x = 1.5, label.y = 40)
比较两个paired sample
compare_means(len~supp, data=ToothGrowth, paired = TRUE)

利用ggpaired()进行可视化
ggpaired(ToothGrowth, x="supp", y="len", color = "supp", line.color = "gray",
line.size = 0.4, palette = "jco")+ stat_compare_means(paired = TRUE)

多组比较
Global test
compare_means(len~dose, data=ToothGrowth, method = "anova")

可视化
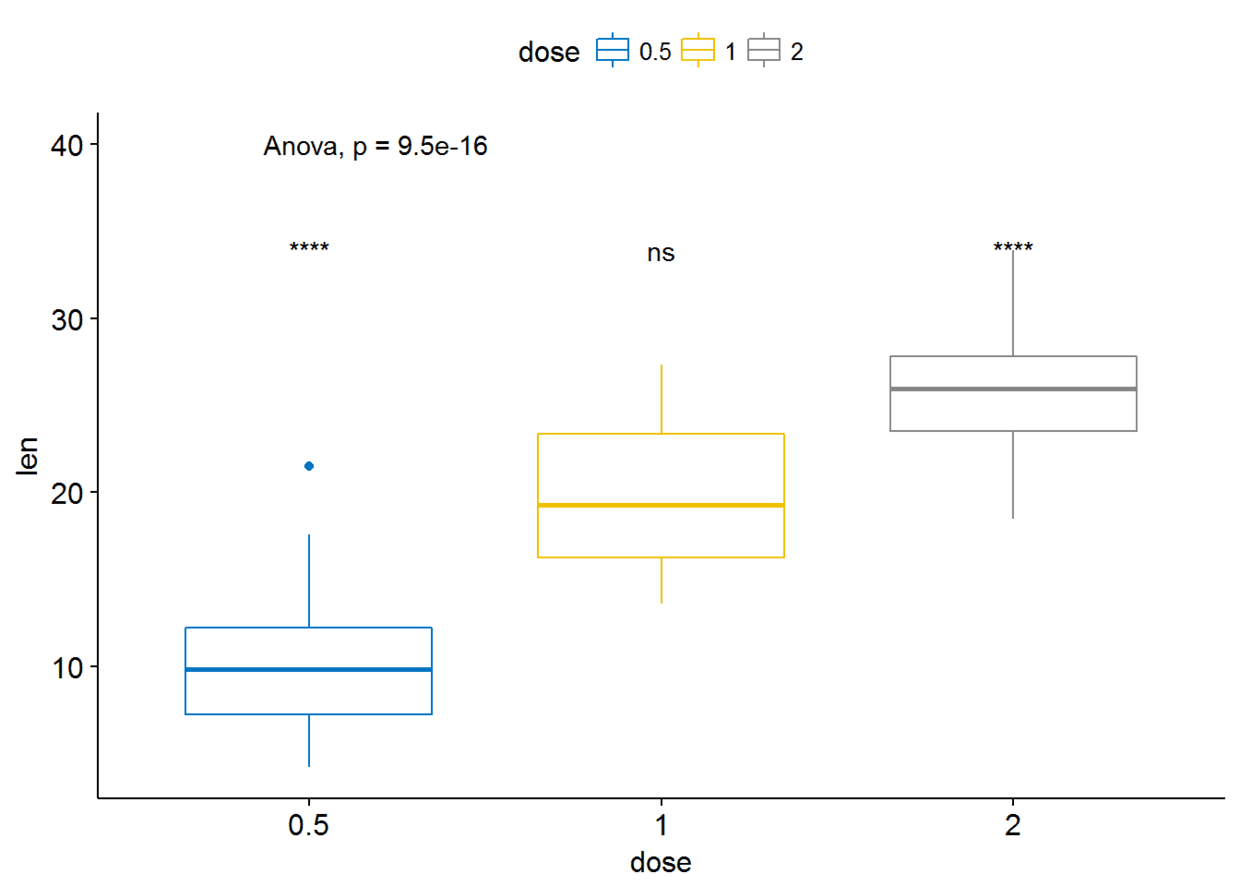
ggboxplot(ToothGrowth, x="dose", y="len", color = "dose", palette = "jco")+
stat_compare_means()
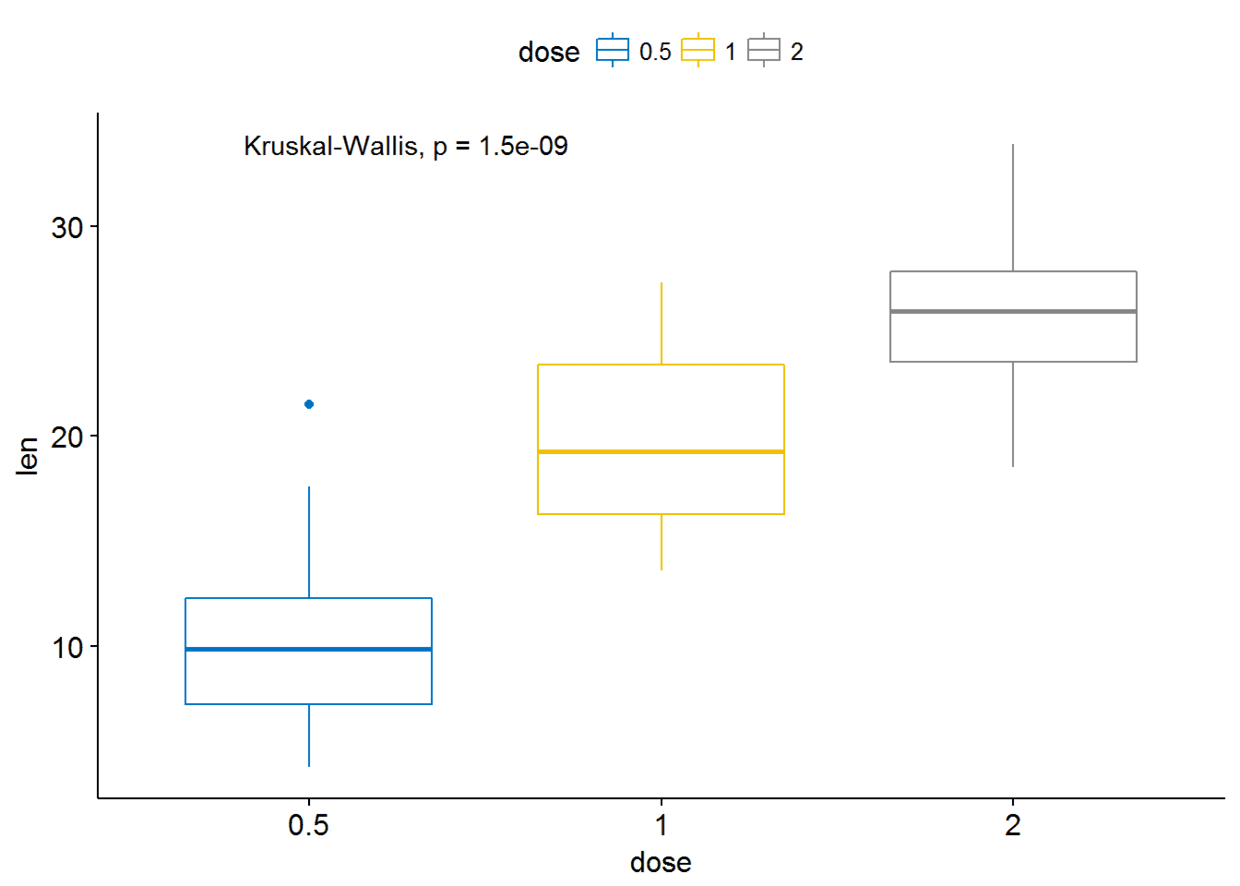
#使用其他的方法
ggboxplot(ToothGrowth, x="dose", y="len", color = "dose", palette = "jco")+
stat_compare_means(method = "anova")

Pairwise comparisons:如果分组变量中包含两个以上的水平,那么会自动进行pairwise test,默认方法为”wilcox.test”
compare_means(len~dose, data=ToothGrowth)

#可以指定比较哪些组
my_comparisons
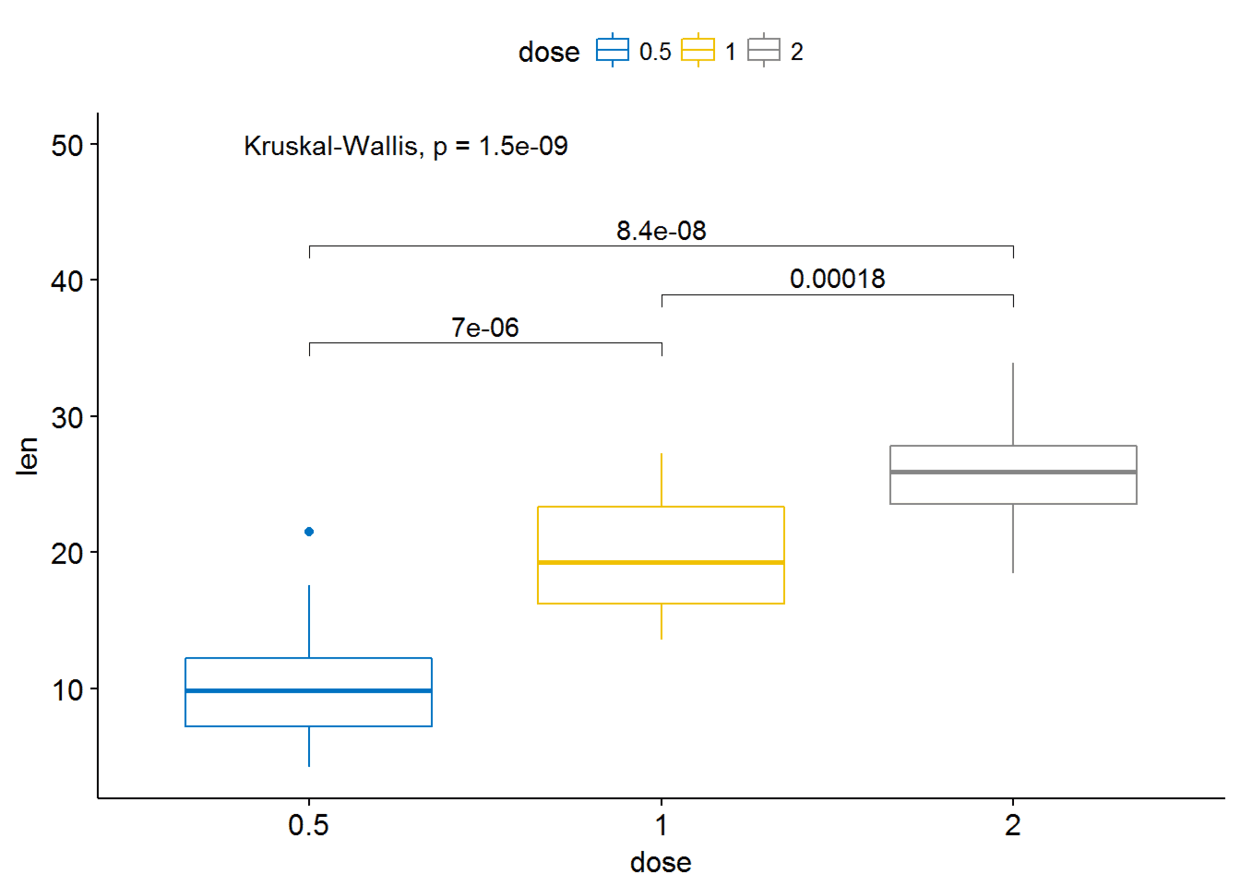
可以通过修改参数label.y来更改标签的位置
ggboxplot(ToothGrowth, x="dose", y="len", color = "dose",palette = "jco")+
stat_compare_means(comparisons=my_comparisons, label.y = c(29, 35, 40))+ # Add pairwise comparisons p-value
stat_compare_means(label.y = 45) # Add global p-value
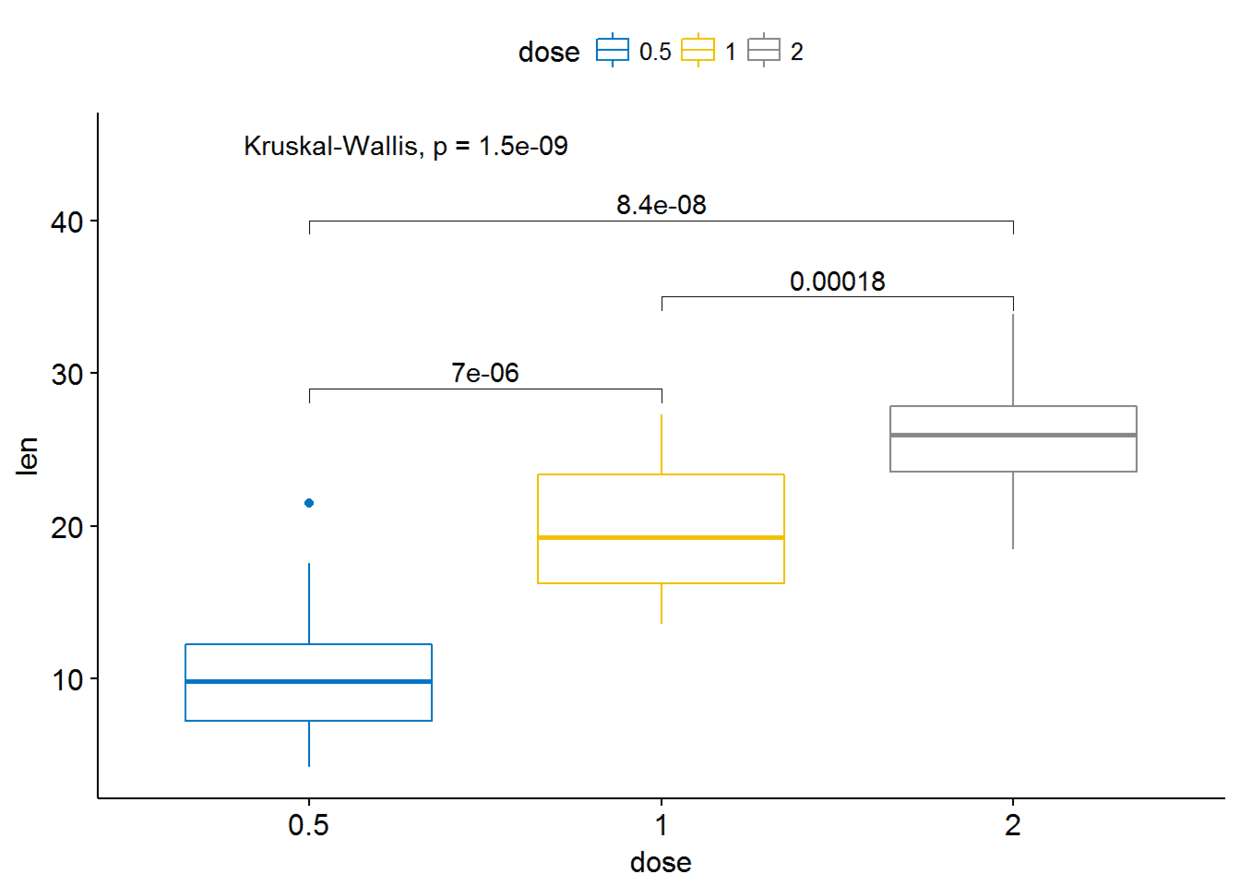
至于通过添加线条来连接比较的两组,这一功能已由包
ggsignif
实现
##设定参考组
compare_means(len~dose, data=ToothGrowth, ref.group = "0.5", #以dose=0.5组为参考组
method = "t.test" )

#可视化
ggboxplot(ToothGrowth, x="dose", y="len", color = "dose", palette = "jco")+
stat_compare_means(method = "anova", label.y = 40)+ # Add global p-value
stat_compare_means(label = "p.signif", method = "t.test", ref.group = "0.5") # Pairwise comparison against reference
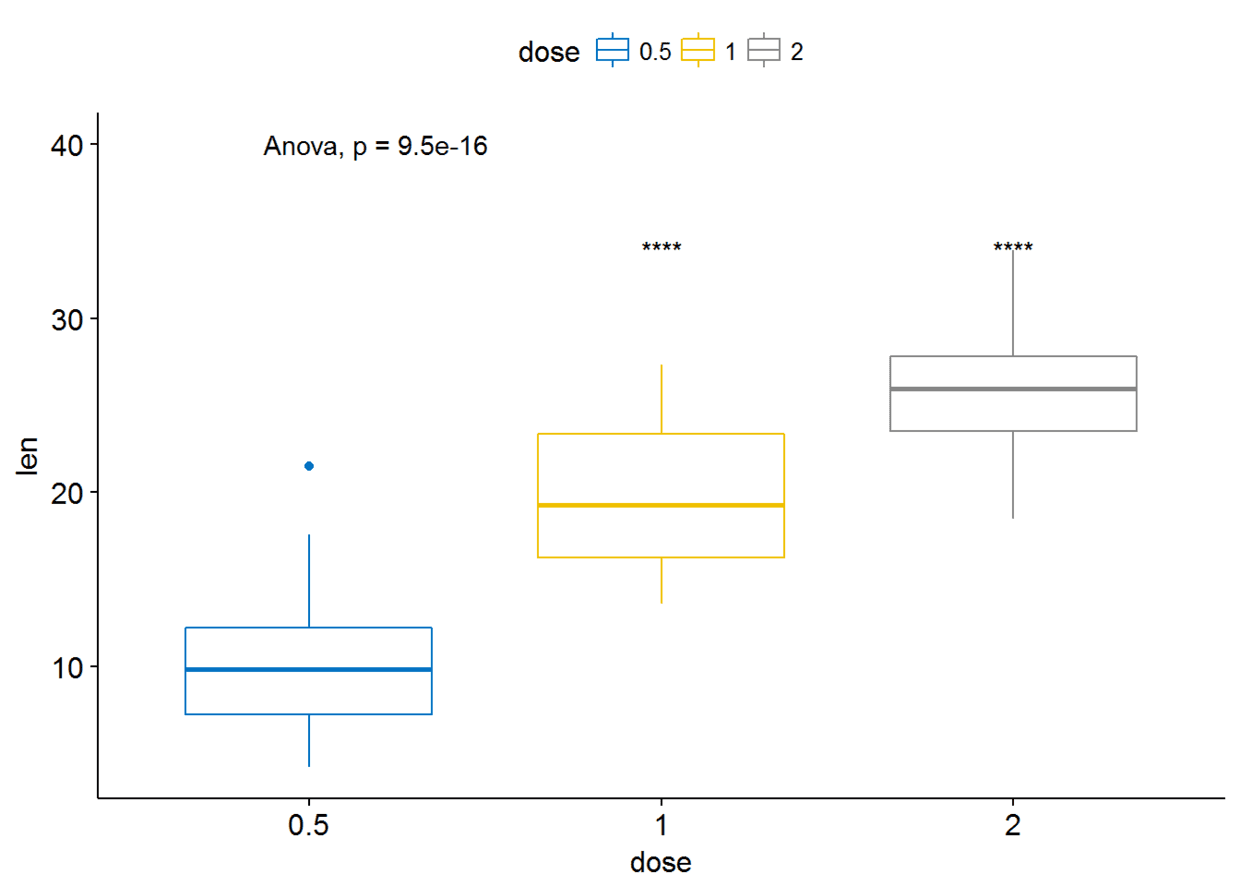 参考组也可以设置为.all.即所有的平均值
参考组也可以设置为.all.即所有的平均值
compare_means(len~dose, data=ToothGrowth, ref.group = ".all.", method = "t.test")

#可视化
ggboxplot(ToothGrowth, x="dose", y="len", color = "dose", palette = "jco")+
stat_compare_means(method = "anova", label.y = 40)+# Add global p-value
stat_compare_means(label = "p.signif", method = "t.test",
ref.group = ".all.")#Pairwise comparison against all
接下来利用
survminer
包中的数据集
myeloma
来讲解一下为什么有时候我们需要将ref.group设置为.all.
library(survminer)#没安装的先安装再加载
data("myeloma")
head(myeloma)
我们将根据患者的分组来绘制
DEPDC1
基因的表达谱,看不同组之间是否存在显著性的差异,我们可以在7组之间进行比较,但是这样的话组间比较的组合就太多了,因此我们可以将7组中每一组与全部平均值进行比较,看看
DEPDC1
基因在不同的组中是否过表达还是低表达。
compare_means(DEPDC1~molecular_group, data = myeloma, ref.group = ".all.", method = "t.test")

#可视化DEPDC1基因表达谱
ggboxplot(myeloma, x="molecular_group", y="DEPDC1",
color = "molecular_group", add = "jitter", legend="none")+
rotate_x_text(angle = 45)+
geom_hline(yintercept = mean(myeloma$DEPDC1), linetype=2)+# Add horizontal line at base mean
stat_compare_means(method = "anova", label.y = 1600)+ # Add global annova p-value
stat_compare_means(label = "p.signif", method = "t.test", ref.group = ".all.")# Pairwise comparison against all
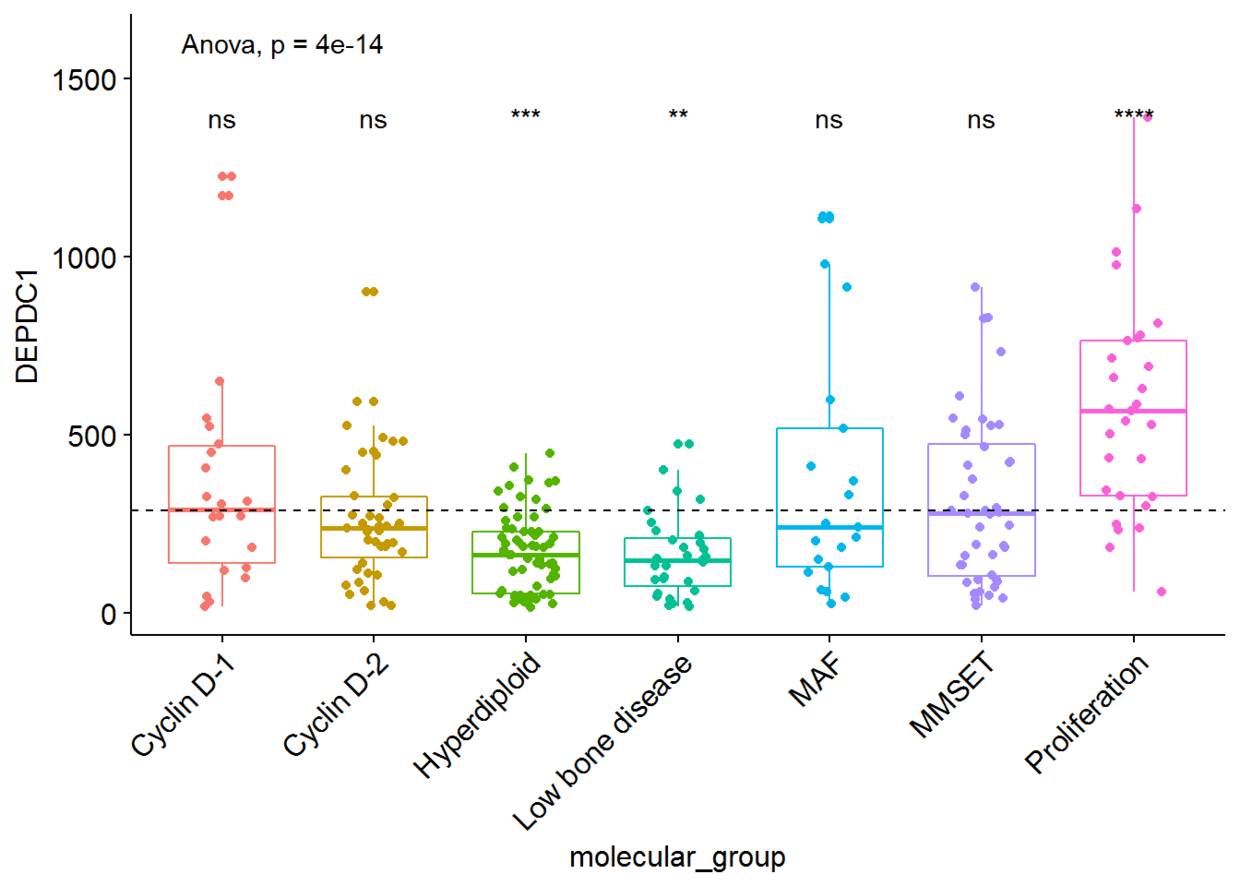
从图中可以看出,DEPDC1基因在Proliferation组中显著性地过表达,而在Hyperdiploid和Low bone disease显著性地低表达
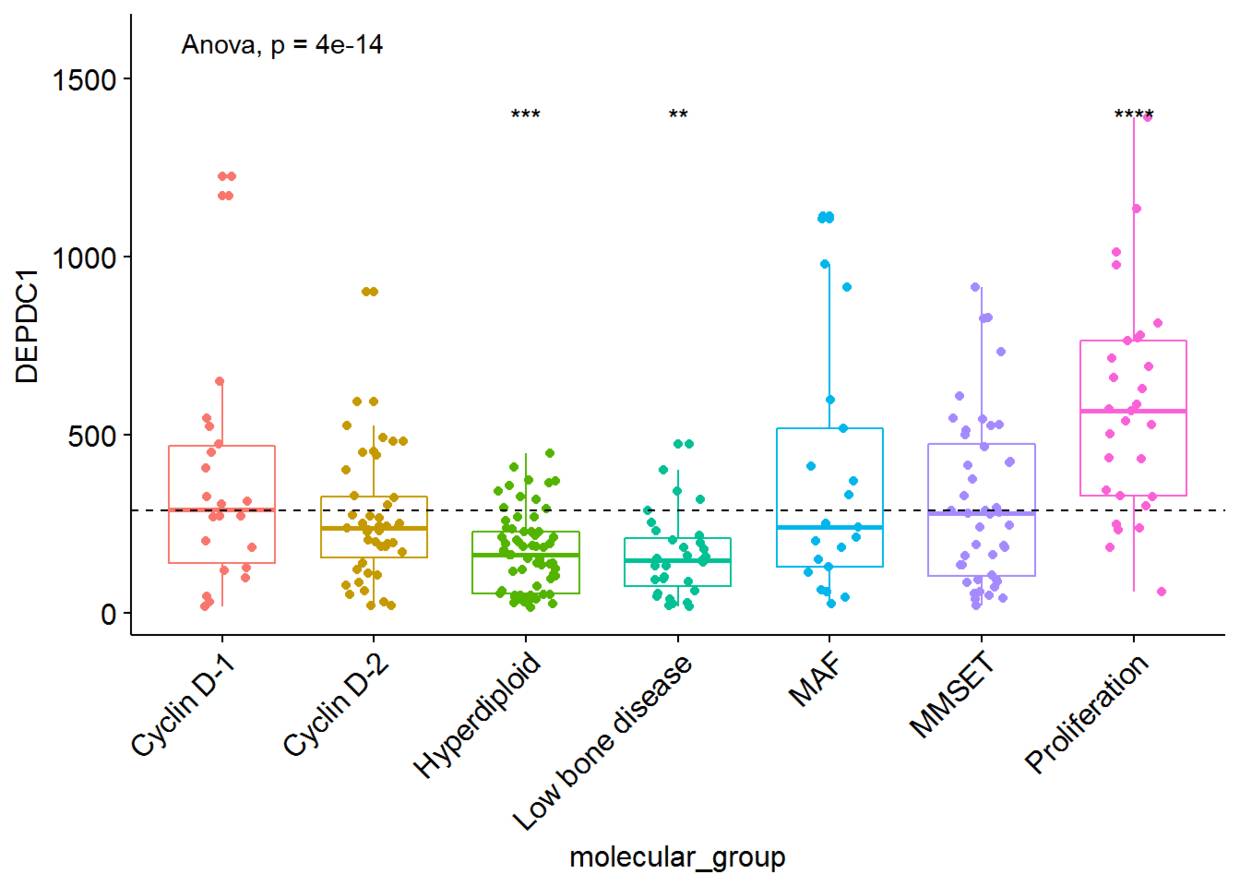
我们也可以将非显著性标记ns去掉,只需要将参数hide.ns=TRUE
ggboxplot(myeloma, x="molecular_group", y="DEPDC1",
color = "molecular_group", add = "jitter", legend="none")+
rotate_x_text(angle = 45)+
geom_hline(yintercept = mean(myeloma$DEPDC1), linetype=2)+# Add horizontal line at base mean
stat_compare_means(method = "anova", label.y = 1600)+ # Add global annova p-value
stat_compare_means(label = "p.signif", method = "t.test", ref.group = ".all.", hide.ns = TRUE)# Pairwise comparison against all
多个分组变量
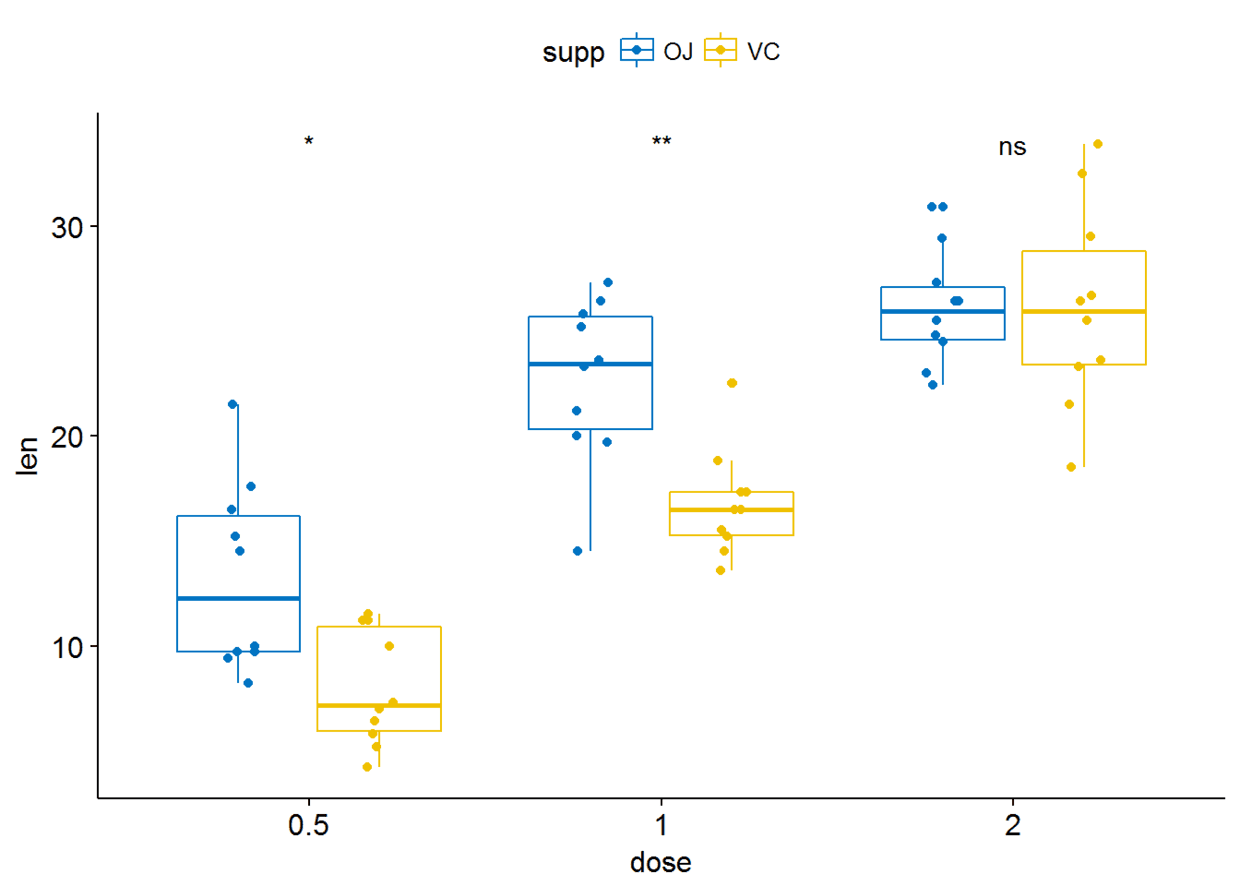
按另一个变量进行分组之后进行统计检验,比如按变量dose进行分组:
compare_means(len~supp, data=ToothGrowth, group.by = "dose")
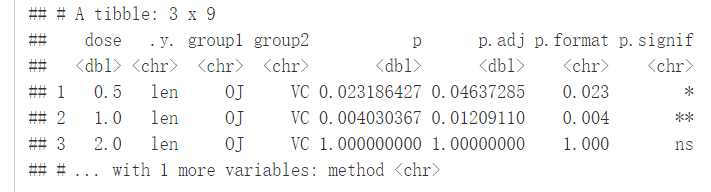
#可视化
p
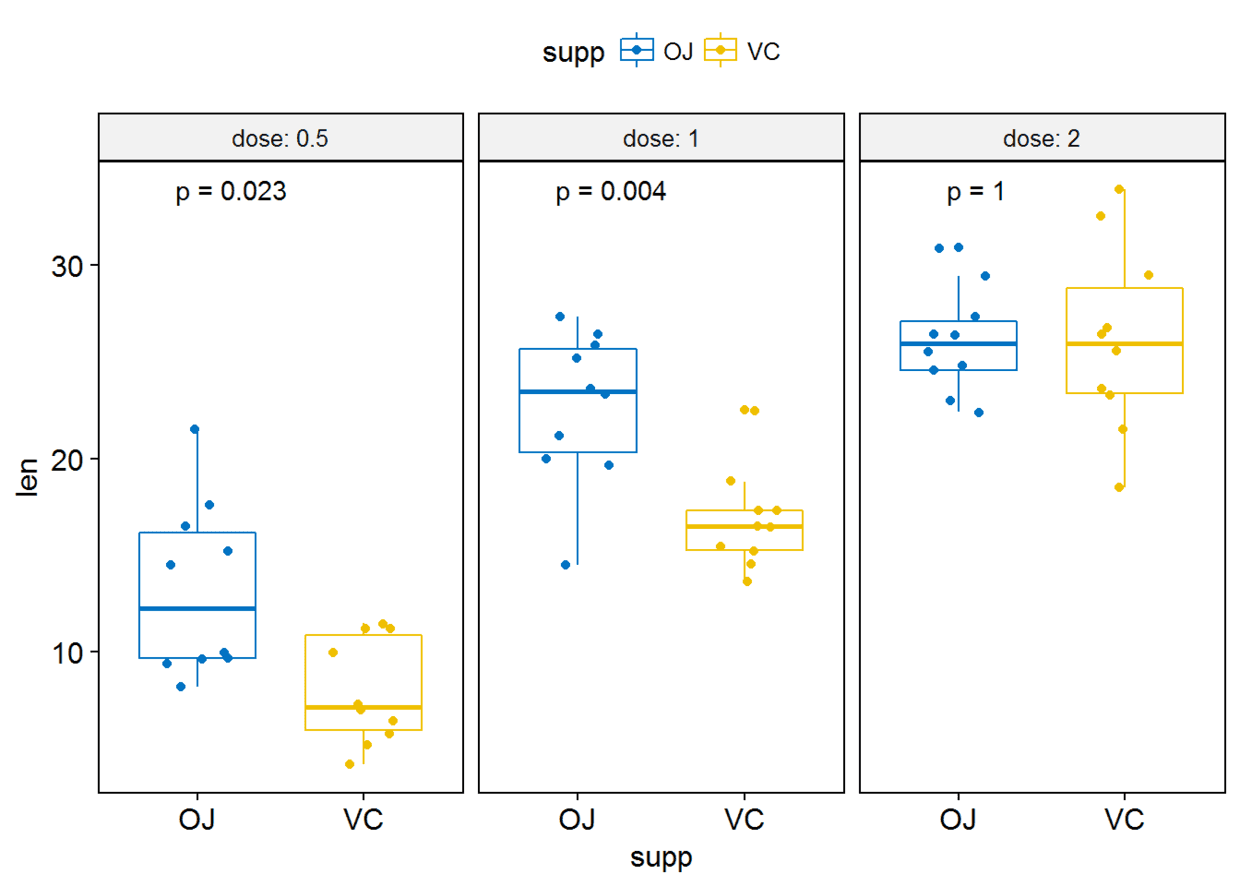
#label绘制显著性水平
p+stat_compare_means(label = "p.signif", label.x = 1.5)

#将所有箱线图绘制在一个panel中
p
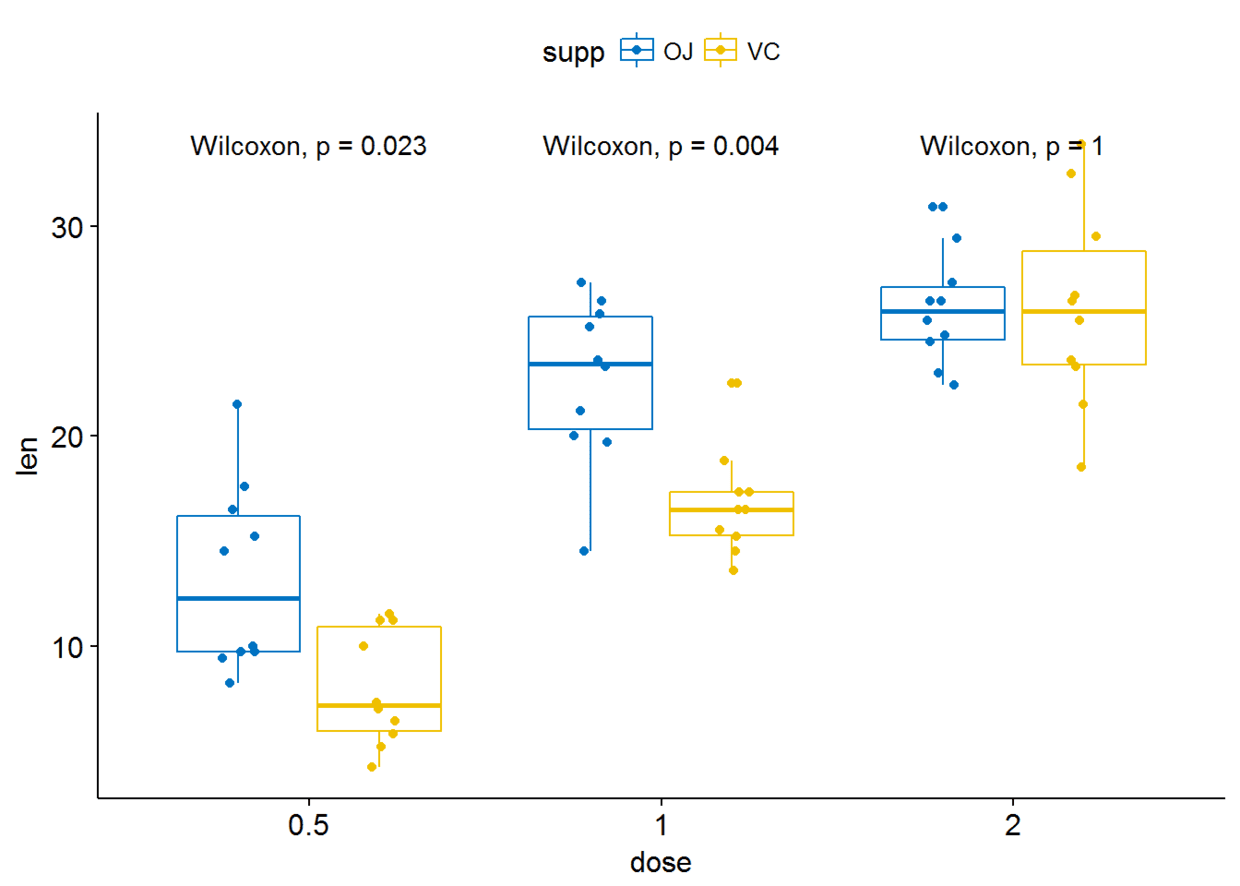
#只显示p-value
p+stat_compare_means(aes(group=supp), label = "p.format")
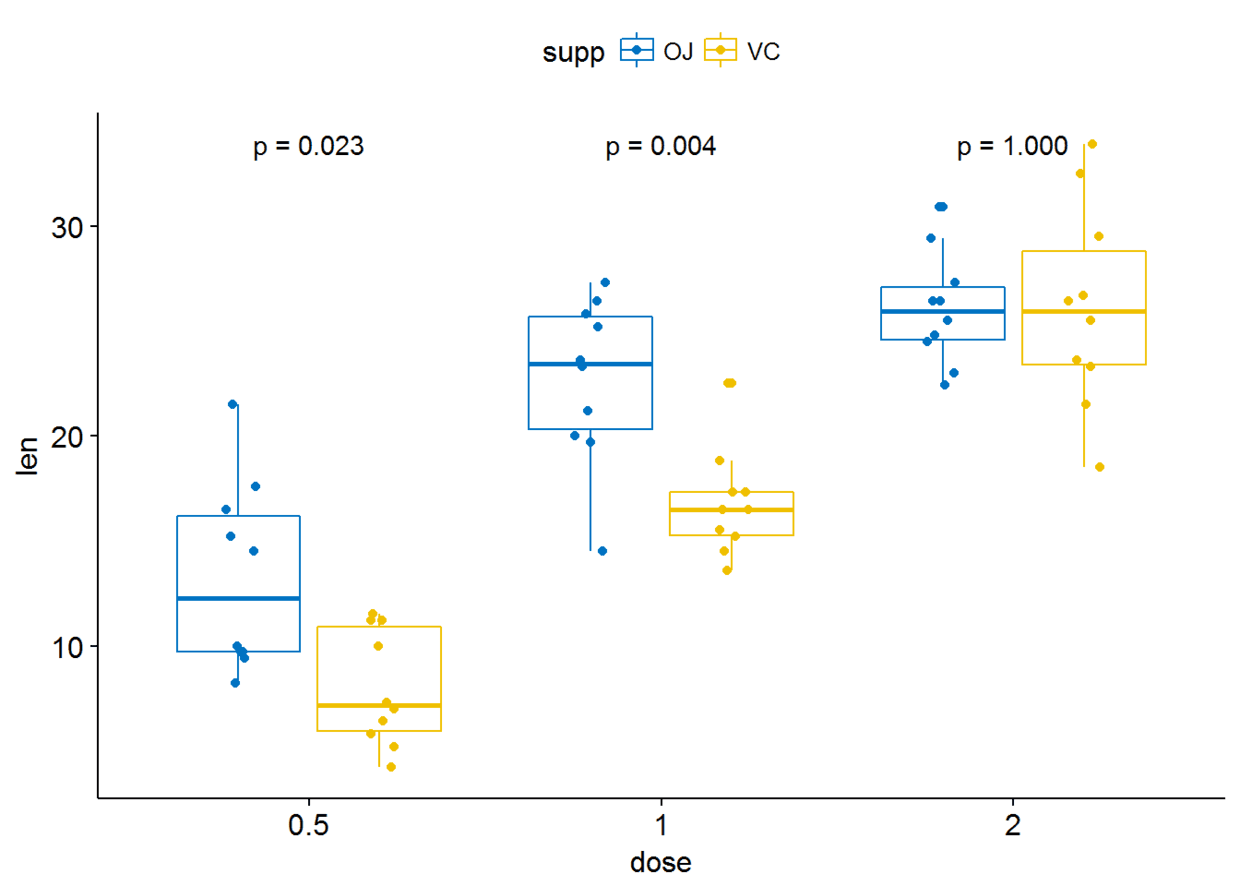
#显示显著性水平
p+stat_compare_means(aes(group=supp), label = "p.signif")
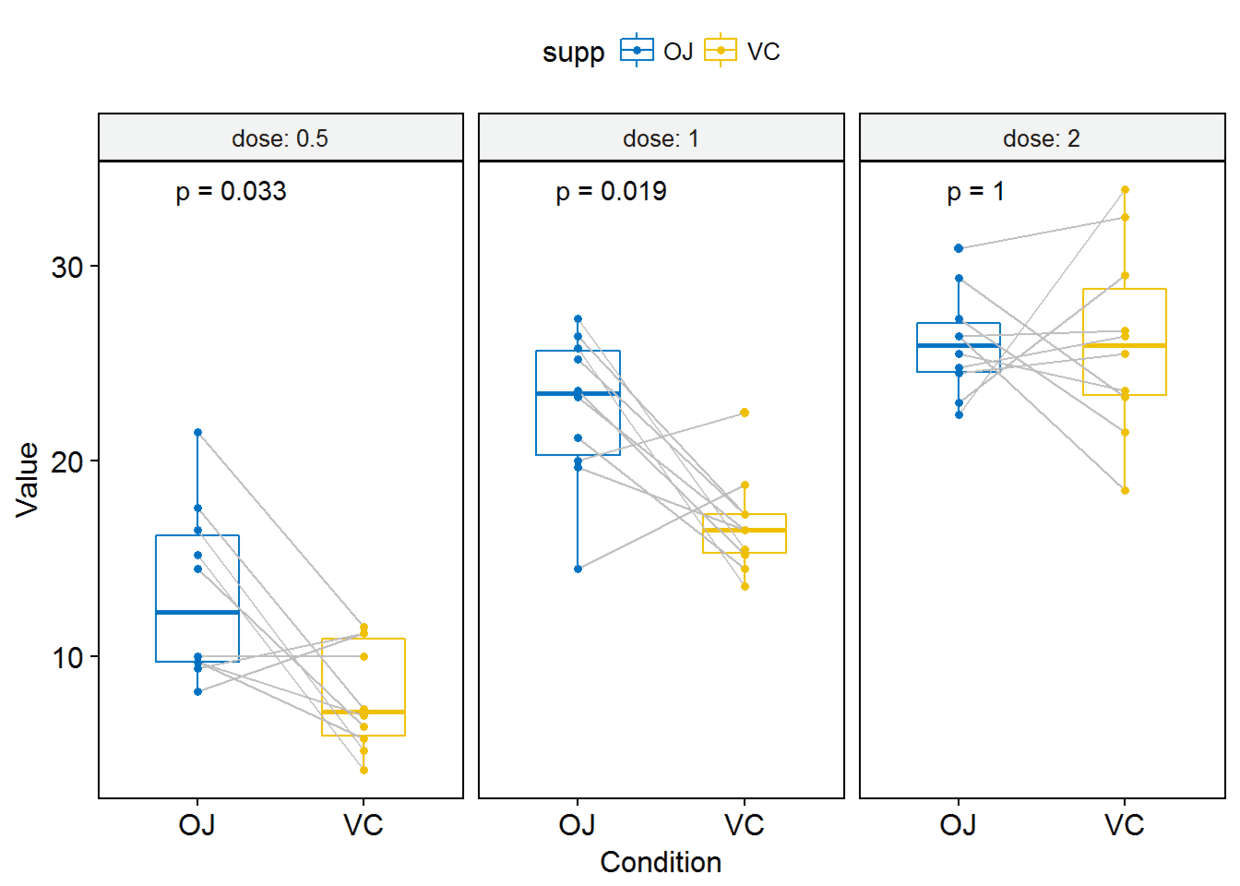
进行paired sample检验
compare_means(len~supp, data=ToothGrowth, group.by = "dose", paired = TRUE)

#可视化
p
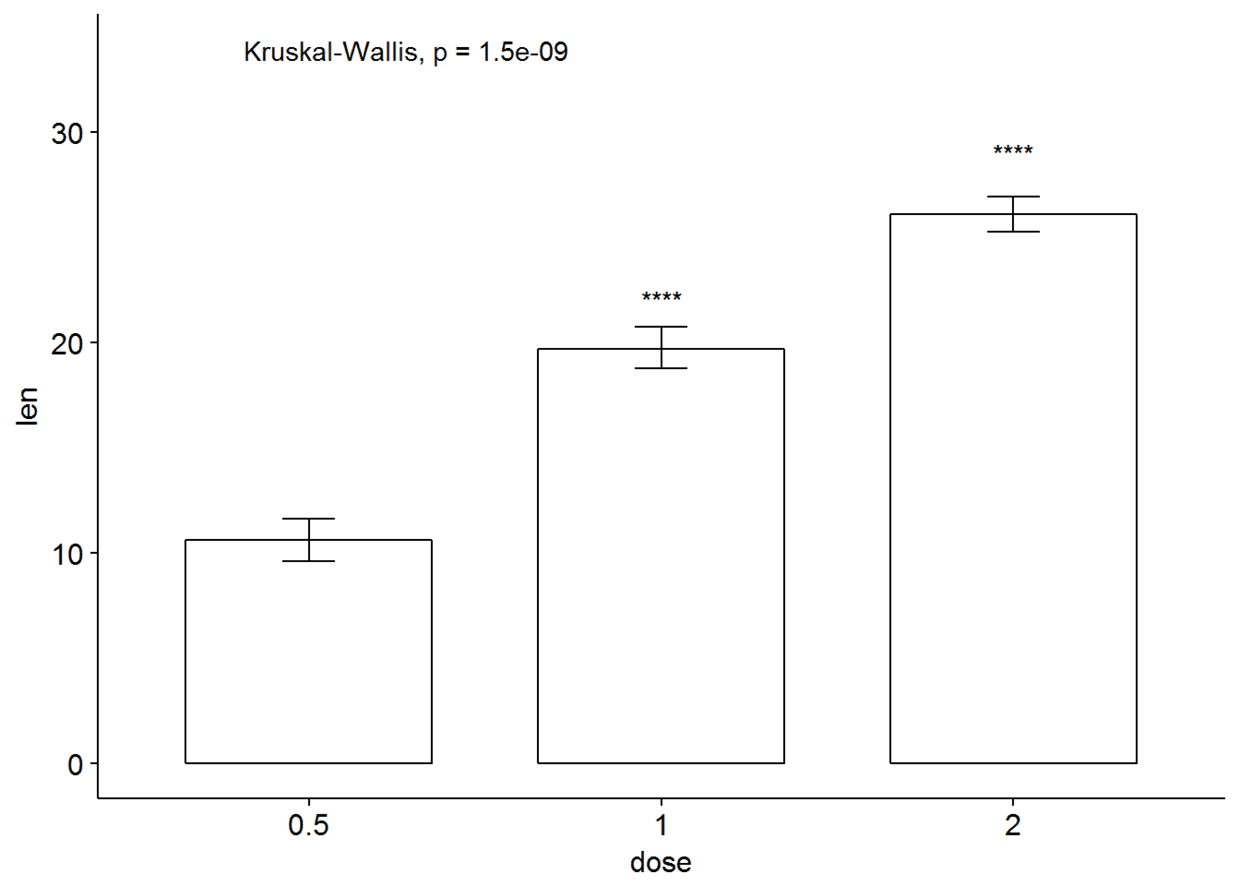
其他图形
条形图与线图(一个分组变量)
#有误差棒的条形图,实际上我以前的文章里有纯粹用ggplot2实现
ggbarplot(ToothGrowth, x="dose", y="len", add = "mean_se")+
stat_compare_means()+
stat_compare_means(ref.group = "0.5", label = "p.signif", label.y = c(22, 29))
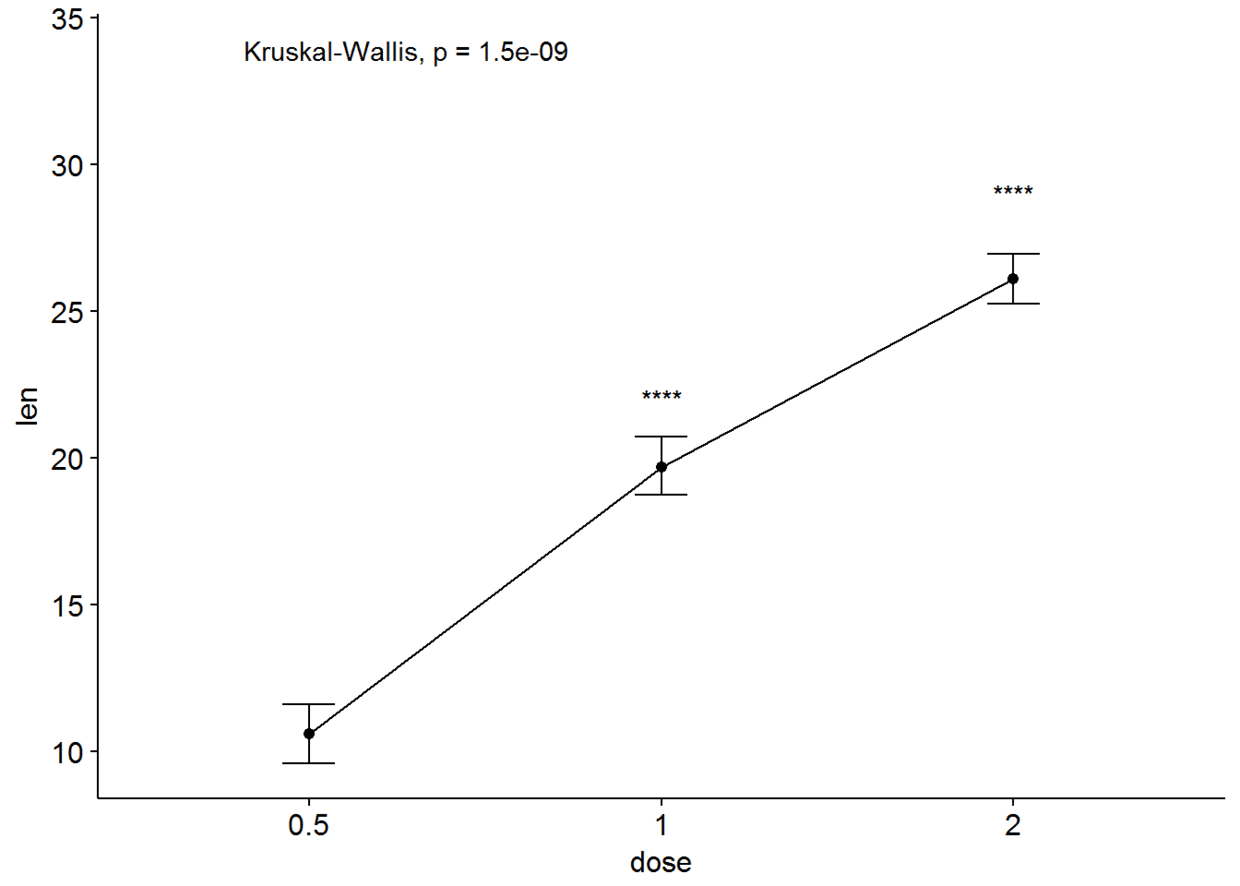
#有误差棒的线图
ggline(ToothGrowth, x="dose", y="len", add = "mean_se")+
stat_compare_means()+
stat_compare_means(ref.group = "0.5", label = "p.signif", label.y = c(22, 29))
条形图与线图(两个分组变量)
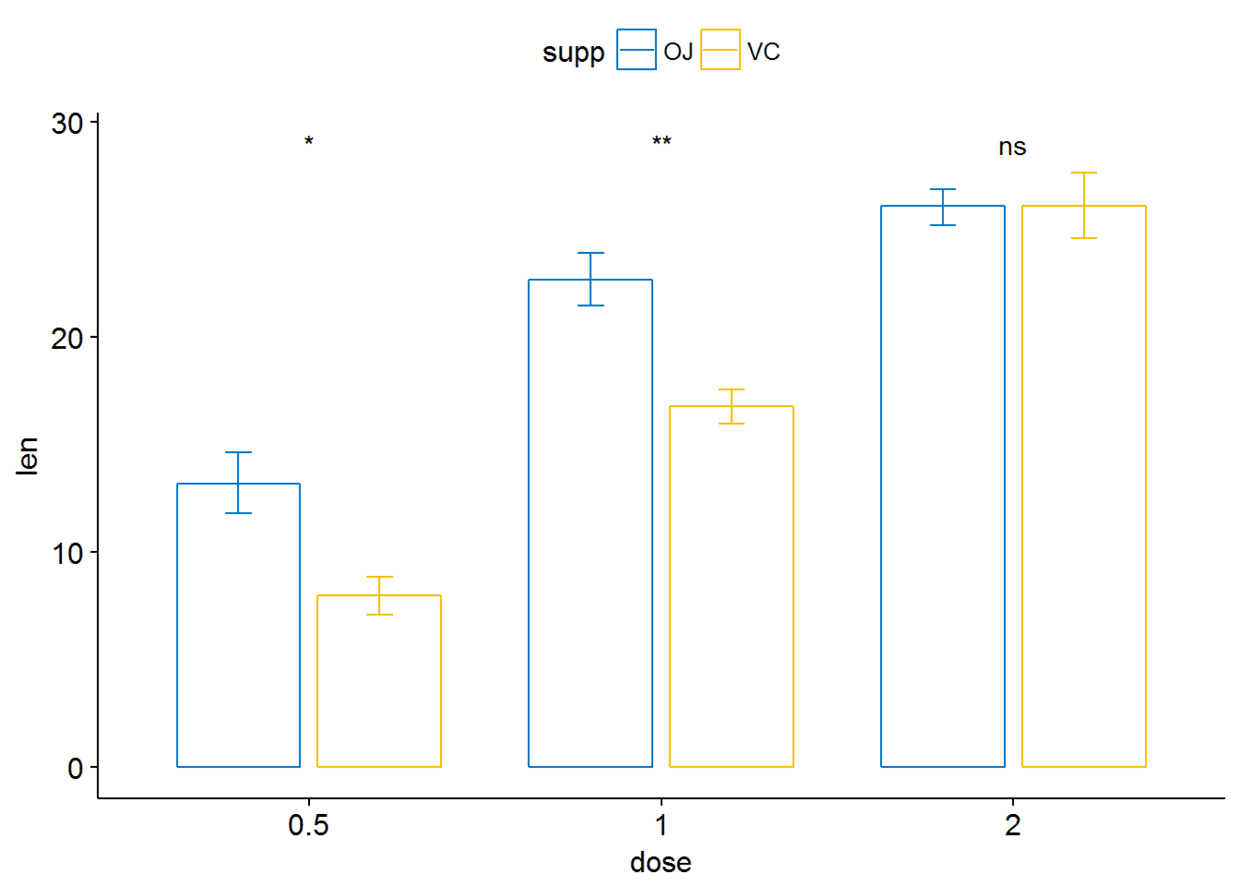
ggbarplot(ToothGrowth, x="dose", y="len", add = "mean_se", color = "supp",
palette = "jco", position = position_dodge(0.8))+
stat_compare_means(aes(group=supp), label = "p.signif", label.y = 29)
ggline(ToothGrowth, x="dose", y="len", add = "mean_se", color = "supp",
palette = "jco")+
stat_compare_means(aes(group=supp), label = "p.signif", label.y = c(16, 25, 29))
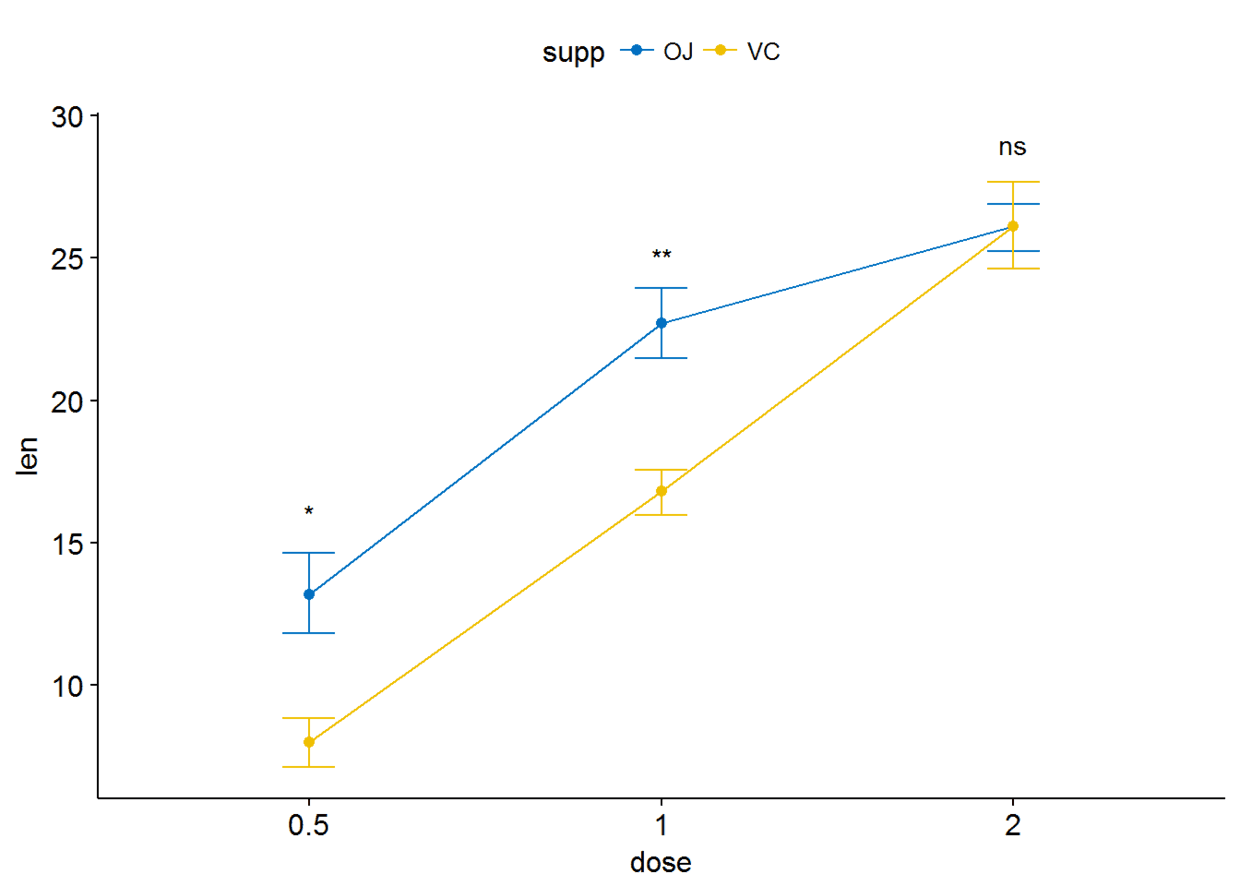
Sessioninfo
sessionInfo()
## R version 3.4.0 (2017-04-21)
## Platform: x86_64-w64-mingw32/x64 (64-bit)
## Running under: Windows 8.1 x64 (build 9600)
##
## Matrix products: default
##
## locale:
## [1] LC_COLLATE=Chinese (Simplified)_China.936
## [2] LC_CTYPE=Chinese (Simplified)_China.936
## [3] LC_MONETARY=Chinese (Simplified)_China.936
## [4] LC_NUMERIC=C
## [5] LC_TIME=Chinese (Simplified)_China.936
##
## attached base packages:
## [1] stats graphics grDevices utils datasets methods base
##
## other attached packages:
## [1] survminer_0.4.0 ggpubr_0.1.3 magrittr_1.5 ggplot2_2.2.1
##
## loaded via a namespace (and not attached):
## [1] Rcpp_0.12.11 compiler_3.4.0 plyr_1.8.4
## [4] tools_3.4.0 digest_0.6.12 evaluate_0.10
## [7] tibble_1.3.3 gtable_0.2.0 nlme_3.1-131
## [10] lattice_0.20-35 rlang_0.1.1 Matrix_1.2-10
## [13] psych_1.7.5 ggsci_2.4 DBI_0.6-1
## [16] cmprsk_2.2-7 yaml_2.1.14 parallel_3.4.0
## [19] gridExtra_2.2.1 dplyr_0.5.0 stringr_1.2.0
## [22] knitr_1.16 survMisc_0.5.4 rprojroot_1.2
## [25] grid_3.4.0 data.table_1.10.4 KMsurv_0.1-5
## [28] R6_2.2.1 km.ci_0.5-2 survival_2.41-3
## [31] foreign_0.8-68 rmarkdown_1.5 reshape2_1.4.2
## [34] tidyr_0.6.3 purrr_0.2.2.2 splines_3.4.0
## [37] backports_1.1.0 scales_0.4.1 htmltools_0.3.6
## [40] assertthat_0.2.0 mnormt_1.5-5 xtable_1.8-2
## [43] colorspace_1.3-2 ggsignif_0.2.0 labeling_0.3
## [46] stringi_1.1.5 lazyeval_0.2.0 munsell_0.4.3
## [49] broom_0.4.2 zoo_1.8-0

R语言可视化学习笔记之ggrepel包
【重磅】史上最全的论文图表基本规范
关于学术论文Figures,你不能不知道的秘密
优雅的操纵json数据地图素材——打破地理信息可视化的孤岛
用R-Shiny打造一个美美的在线App
shiny动态仪表盘——360度全空间无死角拖拉换肤功能的旋转地球
如需转载请联系EasyCharts团队!
送福利啦!
☑
长按文末二维码,关注
EasyCharts
公众号;
☑
加入QQ群,可以在群文件获取
“Excel商业图表修炼秘笈之基础篇-大纲”
;
☑
加入QQ群,可以在群文件获取
《Excel数据之美》试读样章
、
与书籍配套的Excel源文件
和
EasyCharts插件
;

在公众号中回复“
买书
”,即可收到购买链接哦!
我们EasyCharts团队在网易云课堂等你来上课哦,长按下面的二维码就可进入网易学习课堂。本课程定价为
19.9
。

简介
真正的高手,不是会制作高难度的图表,而是能把最平常的图表绘制出商务范!
小菜鸟,老司机,都不容错过本课程哦!
1.
这是Excel史上最全的基础图表类型讲解
;本课程重点讲解了23个基础图表案例,包括Excel自动生成的柱形图,条形图,折线图,面积图,散点图,饼图,圆环图、雷达图,表格,卡片等常用商业图表。
2.
这是Excel史上最全的商业图表风格学习大全
;本课程提供了5种商业图表风格的图表,包括《商业周刊》风格,《华尔街日报》风格1和2,《经济学人》风格1和2,共5种经典商业杂志图表的风格。
3. 本课程包括了150多张张商业图表演示Excel源文件
。每个基础图表案例至少提供6种以上不同的图表风格演示,供读者选择与学习,可以满足不同人群的审美需求。






