箱线图 - 一步绘制
绘图时通常会碰到两个头疼的问题:
-
有时需要绘制很多的图,唯一的不同就是输入文件,其它都不需要修改。如果用R脚本,需要反复替换文件名,繁琐又容易出错。 (R也有命令行参数,不熟,有经验的可以尝试下)
-
每次绘图都需要不断的调整参数,时间久了不用,就忘记参数怎么设置了;或者调整次数过多,有了很多版本,最后不知道用哪个了。
为了简化绘图、维持脚本的一致,我用
bash
对绘图命令做了一个封装,通过配置修改命令行参数,生成相应的绘图脚本,然后再绘制。
首先把测试数据存储到文件中方便调用。数据矩阵存储在
boxplot.normal.data
、
sampleGroup
和
boxplot.melt.data
文件中 (TAB键分割,内容在文档最后。如果你手上有自己的数据,也可以拿来用)。
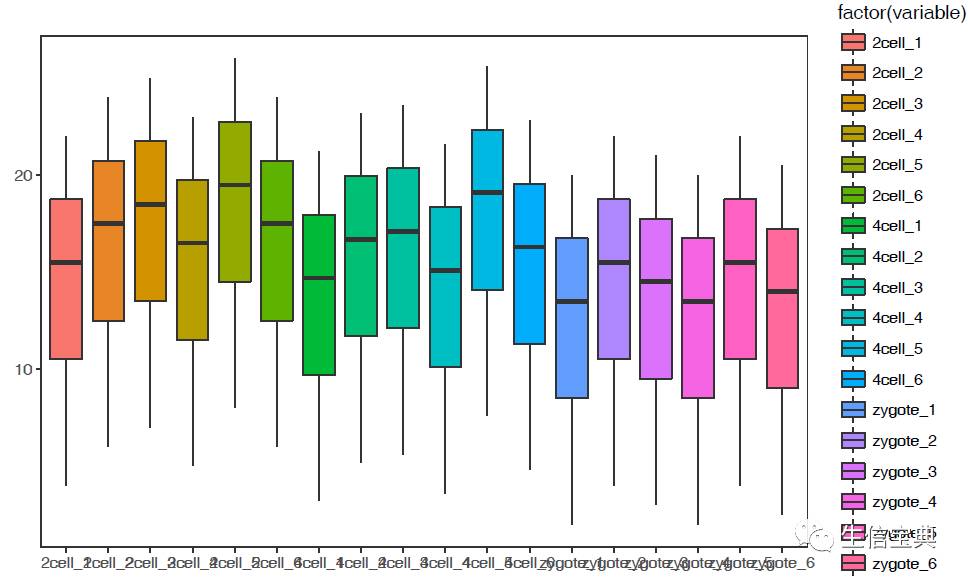
使用正常矩阵默认参数绘制箱线图
# -f: 指定输入的矩阵文件,第一列为行名字,第一行为header
列数不限,列名字不限;行数不限,行名字默认为文本
sp_boxplot.sh -f boxplot.normal.data
箱线图出来了,但有点小乱。
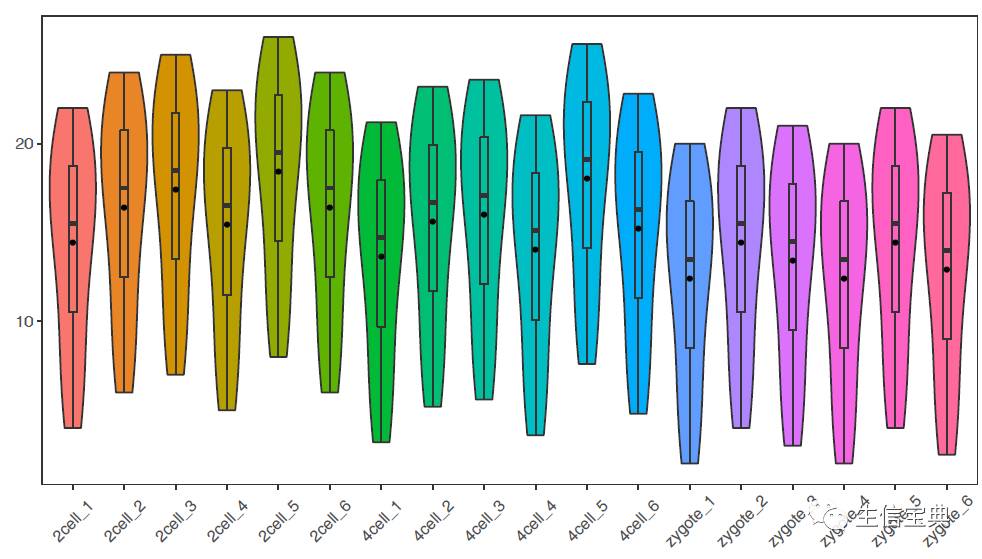
# -f: 指定输入的矩阵文件,第一列为行名字,第一行为header
列数不限,列名字不限;行数不限,行名字默认为文本
# -P: none, 去掉legend (uppercase P)
# -b: X-axis旋转45度
# -V: TRUE 绘制小提琴图
sp_boxplot.sh -f boxplot.normal.data -P none -b 45 -V TRUE
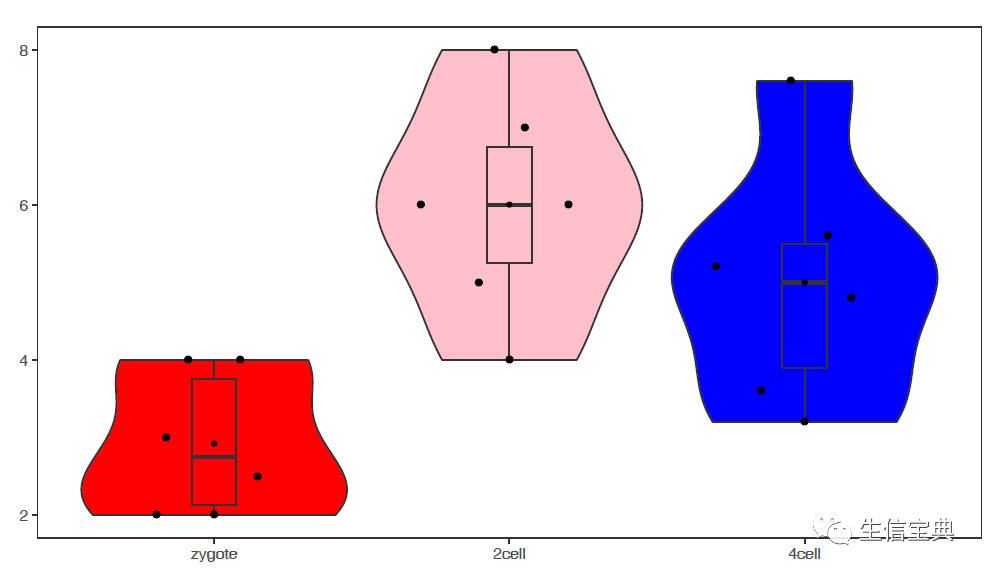
绘制单个基因的小提琴图加抖动图
# -q: 指定某一行的名字,此处为基因名,绘制基因A的表达图谱
# -Q: 指定样本分组,绘制基因A在不同样品组的表达趋势
# -F Group: sampleGroup中第二列的名字,指代分组信息,根据需要修改
# -J TRUE: 绘制抖动图 jitter plot
# -L: 设置X轴样品组顺序
# -c TRUE -C "'red', 'pink', 'blue'": 指定每个箱线图的颜色
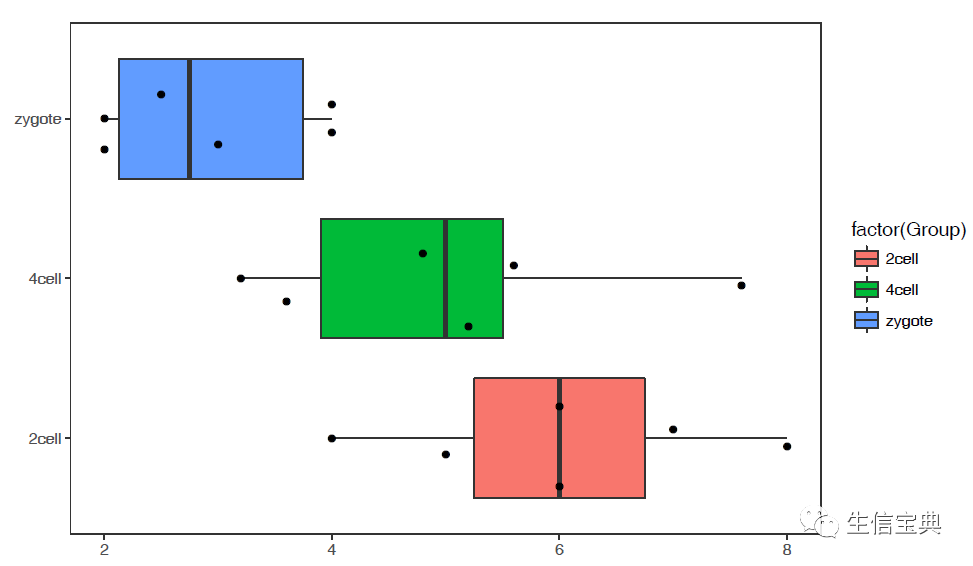
sp_boxplot.sh -f boxplot.normal.data -q A -Q sampleGroup -F Group -V TRUE -J TRUE -L "'zygote','2cell','4cell'" -c TRUE -C "'red', 'pink', 'blue'" -P none
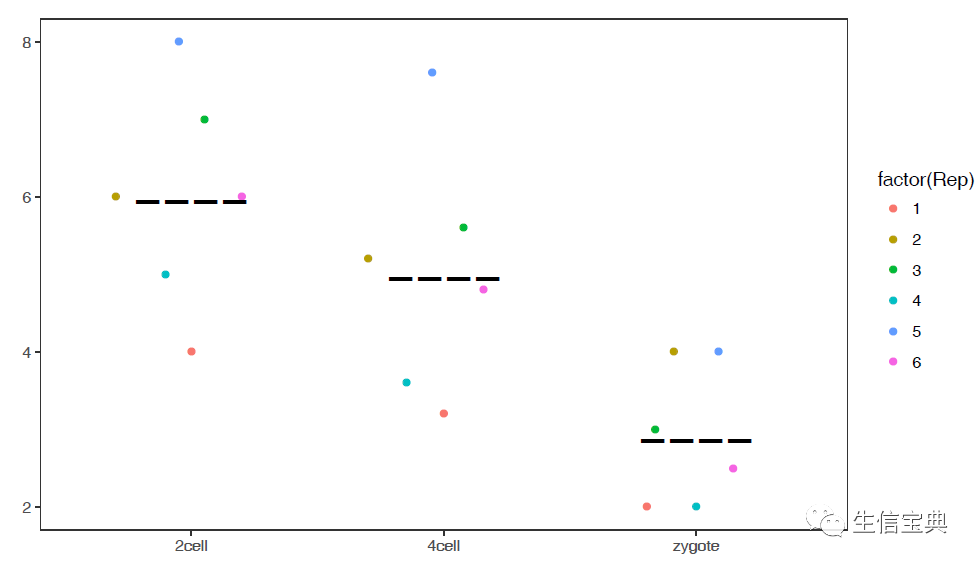
 使用melted矩阵默认参数绘箱线图
使用melted矩阵默认参数绘箱线图
# -f: 指定输入文件
# -m TRUE: 指定输入的矩阵为melted format
# -d Expr:指定表达值所在的列
# -F Rep: 指定子类所在列,也就是legend
# -a Group:指定X轴分组信息
# -j TRUE: jitter plot
sp_boxplot.sh -f boxplot.melt.data -m TRUE -d Expr -F Rep -a Group -j TRUE
# 如果没有子类,则-a和-F指定为同一值
# -R TRUE: 旋转boxplot
sp_boxplot.sh -f boxplot.melt.data -m TRUE -d Expr -a Group -F Group -J TRUE -R TRUE
参数中最需要注意的是
引号
的使用:
为了推广,也为了激起大家的热情,如果想要
sp_boxplot.sh
脚本的,还需要劳烦大家动动手,转发此文章到朋友圈,并留言索取。
也希望大家能一起开发,完善功能。
R绘图学习
R语言学习 - 入门环境Rstudio
R语言学习 - 热图绘制 (heatmap)
R语言学习 - 基础概念和矩阵操作
R语言学习 - 热图美化
R语言学习 - 热图简化
R语言学习 - 线图绘制
R语言学习 - 线图一步法
文章集锦
Linux学习 R统计绘图 Python教程 Perl学习
生信傻瓜 NGS持续更新中 (链接失效,点击菜单知识库查看)
长按关注生信宝典

长按关注宏基因组

测试数据
Name 2cell_1 2cell_2 2cell_3 2cell_4 2cell_5 2cell_6 4cell_1 4cell_2 4cell_3 4cell_4 4cell_5 4cell_6 zygote_1 zygote_2 zygote_3 zygote_4 zygote_5 zygote_6
A 4 6 7 5 8 6 3.2 5.2 5.6 3.6 7.6 4.8 2 4 3




